Resposta técnica às críticas do Dr. Bucci

Relatamos abaixo a resposta técnica da Dra. Loretta Bolgan às críticas publicadas pelo Dr. Bucci nas análises de Corvelva.
Caro Dr. Bucci,
abaixo, respondo às questões críticas que você levantou em particular em seu artigo publicado em: CattiviScienziati. com
Antes de mais, gostaria de salientar que o uso das tecnologias NGS / HTS (sequenciamento de próxima geração ou sequenciamento de alto rendimento) NÃO é original em substratos complexos de origem biotecnológica, como vacinas.
A tecnologia NGS já foi usada em produtos de vacinas, por exemplo:
- na análise de lotes comerciais da vacina contra rotavírus (Victoria JG, Wang C, Jones MS, Jaing C, McLoughlin K, Gardner S, et al. Ácidos nucleicos virais em vacinas vivas atenuadas: detecção de variantes minoritárias e um vírus adventício. J Virol 2010; 84: 6033–40) permitindo o subsequente bloqueio da comercialização de lotes contaminados com circovírus suíno tipo 1 (PCV1), apesar de ter passado anteriormente em todos os testes necessários para o desenvolvimento, ensaios clínicos e produção (Dubin, G.; Toussaint, JF; Cassart, JP; Howe, B.; Boyce, D.; Friedland, L.; Abu-Elyazeed, R.; Poncelet, S.; Han, HH; Debrus, S. Investigação de uma agência reguladora que investiga potenciais tipos de circovírus porcinos 1 contaminação da vacina contra o rotavírus humano, Rotarix: abordagem e resultado Hum. Vaccines Immunother. 2013, 9, 2398-2408).
- na detecção de um novo Rhabdovírus na linhagem celular Sf9 (MH, Galvin TA, Glasner DR, Shaheduzzaman S, Khan AS. Identificação de um novo rabdovírus em linhas celulares de Spodoptera frugiperda. J Virol 2014; 88: 6576–85)
- na identificação do vírus da vacina contra caxumba no cérebro de uma criança imunocomprometida que morreu de encefalite Os dados foram coletados por meio de entrevistas semiestruturadas e entrevistas semi-estruturadas, com o objetivo de avaliar o desempenho dos participantes em relação ao desempenho da equipe. H, Jacques TS, Schepelmann S, Qasim W, Breuer J. O sequenciamento profundo revela a persistência do vírus da vacina contra caxumba associado a células na encefalite crônica.Acta Neuropathol.2017 Jan; 133 (1): 139-147. Doi: 10.1007 / s00401- 016-1629-y. Epub 2016, 21 de outubro de 27770235 PubMed PMID: XNUMX).
Também no trabalho colaborativo de 2017 'Um estudo multicêntrico para avaliar o desempenho do sequenciamento de alto rendimento para detecção de vírus' (A Khan AS, Ng SHS, Vandeputte O, Aljanahi A, Deyati A, Cassart JP, Charlebois RL, Taliaferro LP. A Estudo multicêntrico para avaliar o desempenho do sequenciamento de alto rendimento para detecção de vírus. MSphere. 2017, 13 de setembro; 2 (5) .pii: e00307-17. Doi: 10.1128 / mSphere.00307-17. ECollection 2017 setembro-outubro. PubMed PMID : 28932815; PubMed Central PMCID: PMC5597969), destaca-se como análises realizadas com diferentes instrumentos HTS, com diferentes protocolos de preparação de amostras e análise de dados, em amostras mimetizando materiais biológicos complexos, têm mostrado sensibilidade semelhante na detecção de vírus em 3 vários workshops.
Finalmente, no 'Relatório da conferência internacional sobre sequenciamento de próxima geração para detecção adventícia de vírus em produtos biológicos' (Khan AS, Benetti L, Blumel J, Deforce D, Egan WM, Knezevic I, Krause PR, Mallet L, Mayet D, Minor PD O objetivo deste estudo foi avaliar a eficácia de um agente antimicrobiano na detecção de vírus adventícios em produtos biológicos. PubMed PMID: 2018), relatório de uma conferência internacional realizada em Rockville (MD) de 55 a 1 de outubro de 16, co-organizada pela IABS (Aliança Internacional para Padronização Biológica) e pela FDA (US Food and Drug Administration), em Com a participação de cento e vinte e oito cientistas de 10.1016 países diferentes, incluindo os pesquisadores Glaxo SmithKline, Merck e Sanofi, afirma-se que:
“As principais vantagens do NGS para testes de segurança para detecção de vírus são a abordagem rápida e não direcionada, que pode ser usada em vários substratos e permite detectar uma ampla variedade de vírus, incluindo variantes e novas espécies. ; e que não há necessidade de amplificação específica, enquanto a PCR exige direcionar uma sequência específica "
E ainda:
"As tecnologias HTS estão revelando algumas das limitações atuais de programas para testar materiais biológicos e podem integrar lacunas nesses programas e aumentar a segurança do produto"
E nas conclusões do relatório lemos:
"Esforços contínuos de colaboração e científicos, intercâmbios entre agências reguladoras e outros órgãos públicos, indústria, laboratórios acadêmicos e prestadores de serviços avançarão no campo da NGS com o objetivo de garantir a segurança de produtos orgânicos com impacto na saúde humana e animal"
Respondo abaixo às suas observações, em particular àquelas que nos permitem explicar melhor os dados preliminares que produzimos em alguns lotes do Priorix Tetra.
Observação 1
"É de se perguntar como essa prática de sigilo, contrária a qualquer critério de compartilhamento de dados, pode ser conciliada com os pedidos contínuos de transparência feitos pela associação CORVELVA e pelo presidente da Ordem Nacional de Biólogos em termos de segurança de vacinas: é lícito lançar um alarme, sem fornecer todos os dados necessários para avaliar sua consistência?
Como a comunidade científica e os cidadãos podem avaliar o peso de certas reivindicações, se os dados originais completos são mantidos em segredo, enquanto um promotor público decide se e como proceder com uma ação judicial? "
Resposta 1
Os dados metagenômicos divulgados por Corvelva para o Priorix Tetra (vacina MPRV) e discutidos no relatório publicado em dezembro foram preliminares (uma versão atualizada foi divulgada no site da Corvelva em 23 de janeiro, resultado de uma nova etapa na análise de dados), porque, como já reiteramos em várias ocasiões, os dados divulgados até agora resultam de um processo de pesquisa e desenvolvimento tecnológico iniciado em 2017, com o objetivo de aperfeiçoar e otimizar todo o procedimento, desde o processamento da amostra até a análise de bioinformática. Decidiu-se divulgar os resultados durante o trabalho, à medida que estiverem disponíveis, em absoluta transparência (exatamente o oposto do que é declarado por você como uma 'prática de sigilo'!) E, de qualquer forma, fortemente apoiado pela literatura científica sobre o assunto. 'argumento.
Em nossa opinião, o que divulgamos até agora sobre esta vacina, especialmente em relação à alta quantidade de DNA fetal humano, não é nada novo ou inesperado e muito menos desconhecido para as empresas farmacêuticas.
Observação 2
“É fácil perceber que o total de leituras indicadas no canto superior esquerdo (destacadas em amarelo) é superior a 6 milhões; no entanto, a soma de todas as leituras divididas por classe de organismo é de aproximadamente 5 milhões e meio, com um "déficit" de mais de 700.000 leituras (e uma soma percentual, indicada pela caixa vermelha, igual a 88%). Essa adição simples, repetida em todas as tabelas, faz a pergunta de onde as leituras ausentes terminaram (uma porcentagem que certamente não é desprezível) e por que elas não foram relatadas. A possibilidade de os pesquisadores cometerem um erro permanece claramente aberta "
Resposta 2
Digamos que 700.000 leituras alterem mais ou menos levemente a substância das análises preliminares de triagem realizadas. Sequências ausentes são incluídas no cálculo de sequências 'não atribuídas'. Como já mencionado, os dados não são definitivos e podem haver imprecisões nos relatórios. Tudo será revisado e corrigido à medida que o trabalho avança.
Observação 3
“O genoma do vírus da rubéola, um dos vírus atenuados necessários para conferir imunogenicidade, não estaria presente. A detecção em níveis muito baixos, beirando o ruído estatístico, de um microrganismo na amostra em exame não depende, portanto, da sua ausência, mas do método de identificação não otimizado. A mesma dificuldade idêntica pode ser encontrada para a identificação de qualquer outro genoma, para o qual o método de análise não foi devidamente calibrado; a falta de divulgação do genoma do vírus da rubéola (além disso, um vírus de fita simples encapsulado) é, portanto, atribuível ao método utilizado, sem a necessidade de invocar sua ausência nos lotes de vacina examinados ”
Resposta 3
Sua tese é aceitável. Estamos na fase de pesquisa e desenvolvimento, no entanto, a tecnologia é muito robusta e reconhecida pela comunidade científica que lida com o seqüenciamento profundo para a detecção de vírus em substratos biológicos complexos. Os testes interlaboratoriais e a introdução de padrões apropriados de mistura viral certificada nos permitirão verificar ou refutar a hipótese que você propôs, ou seja, que o método ainda não está otimizado para vírus.
De qualquer forma, o genoma da rubéola foi encontrado no lote em exame, aumentando a profundidade do sequenciamento (114 sequências de extremidade emparelhada com 125 pb de comprimento, de cerca de 260 milhões de seqüências produzidas), conforme descrito no segundo relatório de janeiro de 2019. Também na vacina MMRVax Pro da Merck, analisado em 2017 com o mesmo método, o genoma do vírus da rubéola foi encontrado sem ter que ir a profundidades tão profundas, provando que o método funciona.
Observação 4
“Os genomas de numerosos organismos contaminantes pertencentes a numerosos táxons seriam detectados, incluindo helmintos, bactérias e vírus patogênicos humanos adventícios. Há também um problema adicional nas tabelas apresentadas, consistindo na abundante frequência de sequências atribuíveis a vírus integrados no genoma humano (endovírus de várias naturezas) ou em sequências retrovirais conhecidas por serem encontradas no genoma humano normal (é o caso, por exemplo, de sequências retrovirais integrados que podem ser confundidos com HIV) ou no genoma de células embrionárias de frango usadas para a produção da vacina, normalmente encontrados como atribuições falsas a genomas contaminantes no sequenciamento de DNA ou RNA, dependendo da endosquência específica considerada. Em primeiro lugar, existem inúmeras espécies listadas nas tabelas de relatórios, encontradas com base em várias leituras totalmente incluídas no ruído estatístico. 3 ou menos leituras é um procedimento arriscado que leva a um número alto de falsos positivos "
Resposta 4
A versão do relatório divulgada no site da Corvelva em dezembro, à qual você se refere, foi atualizada recentemente com uma versão na qual uma parte dos contaminantes foi validada preliminarmente com software alternativo e depois manualmente. A primeira análise foi deliberadamente realizada sem filtros para destacar todos os sinais possíveis e todos os problemas relacionados a uma análise "aberta". O objetivo do nosso trabalho não é, como reiterado várias vezes, realizar uma análise da liberação do lote, mas realizar uma triagem preliminar e, posteriormente, uma confirmação interlaboratorial dos problemas críticos que surgiram, através do uso de uma tecnologia bem estabelecida em campo. genômica, já aplicada em vacinas e futura também por agências reguladoras e grandes empresas farmacêuticas para aumentar a qualidade e, consequentemente, a segurança do produto.
Se você definir o limite de três leituras (com base em quê?), Poderíamos pelo menos pensar que os sinais de presença de retrovírus endógenos nesta vacina são prováveis (Retrovírus Endógeno Humano K: 3 leituras de 32 pb, correspondendo a 125 pb e HERVH- env 4000: 62 lê, correspondendo a 4 pb), nos dados de RNA-seq, que por definição representam o material transcrito e, portanto, potencialmente ativo.
Em vez disso, concordo com você que as seqüências retrovirais encontradas nos dados do DNA-seq podem ser provírus integrados ao genoma humano, dada a quantidade muito alta de DNA humano na vacina em questão.
Lembro-me que na vacina Attenuvax (vacina contra o sarampo), quatro seqüências cobrindo 4 pb (Victoria JG, Wang C, Jones MS, Jaing C, McLoughlin K, Gardner S, et al., Ácidos nucleicos virais em vacinas vivas atenuadas: detecção de variantes minoritárias e um vírus adventício.J Virol 700; 2010: 84–6033) permitiu detectar pela NGS uma contaminação pelo vírus do vírus da leucose aviária (ALV) pela primeira vez em uma vacina, depois confirmada por PCR aninhado.
Observação 5
"No que diz respeito ao primeiro desses contaminantes em potencial, a bactéria Bradyrhizobium não patogênica fixadora de nitrogênio, sua" aparência "em laboratórios de seqüenciamento é conhecido como um problema relacionado à preparação das amostras a serem sequenciadas, atribuível à contaminação dos kits de purificação de DNA, água e reagentes a serem utilizados. Um problema bem conhecido, no qual, no trabalho de genômica "exploratória", uma amostra de controle, por exemplo, contendo água, é sequenciada paralelamente à amostra em exame "
Resposta 5
Os brancos foram feitos (tanto da extração quanto da biblioteca), mas as bibliotecas não foram obtidas e, portanto, não foi possível executá-las no seqüenciador para verificar exatamente qual é a contaminação do reagente / ambiente. No entanto, estão sendo feitos esforços para tentar entender o que são contaminações 'fisiológicas' e os testes interlaboratoriais também ajudarão a determinar possíveis contaminações bacterianas dependentes de laboratório.
Observação 6
“Quanto aos dois tipos de vermes revelados na análise de seqüenciamento de RNA, é suficiente observar como eles não estão presentes nas análises de sequenciamento de DNA correspondentes, onde eles devem ser muito melhor detectáveis; consequentemente, a presença real das duas espécies aparece como um artefato, que não pode ser confirmado à luz dos mesmos dados de seqüenciamento de DNA apresentados.
À luz das considerações feitas, não é, portanto, possível confirmar a presença de nenhum dos genomas contaminantes relatados, e há pistas fortes que nos levam a pensar na presença de vários falsos positivos ".
Resposta 6
A segunda versão do relatório já forneceu uma primeira validação de alguns organismos encontrados, tanto com software alternativo quanto manualmente.
A avaliação das atribuições incorretas do software Kraken (além disso, um dos softwares mais usados pela comunidade científica para análises metagenômicas de todo o genoma) está sendo usada para desenvolver um pipeline de bioinformática ad hoc para esse tipo de análise, que não requer o uso de outros. inspeção manual e de software (além disso comum no campo da metagenômica para problemas de última geração devido à ausência de bancos de dados específicos e particularmente precisos).
Observação 7
"O DNA humano detectado seria de alto peso molecular e a cobertura do genoma humano seria total, de modo que todo o genoma das células fetais humanas e não partes dele estivessem presentes nos lotes de vacinas examinados."
"Na vacina Priorix Tetra, o DNA genômico humano tem alto peso molecular (> 10.000 pb) e a cobertura sequencial total de todo o genoma humano de referência (HG-19) demonstra que é todo o genoma das células fetais usadas para a cultura do vírus da vacina esteja presente e não apenas porções dela. "
Nenhuma evidência direta é fornecida para a afirmação declarada, sem prejuízo da presença de DNA pesando cerca de 100.000 bases reveladas por eletroforese em gel pelos autores (documentada com uma figura de baixa qualidade no documento CORVELVA, da qual seria aconselhável obter um alto original resolução para avaliar se os dados são apresentados de maneira intacta).
No entanto, os autores esquecem que o DNA de alguns dos vírus atenuados presentes na vacina em questão tem aproximadamente o mesmo tamanho do que eles revelaram no gel (por exemplo, o DNA do vírus da varicela é de 125 kb); portanto, mesmo que você queira vislumbrar traços de DNA de alto peso na imagem de gel apresentada, isso pode ser claramente atribuído ao DNA dos vírus atenuados presentes na vacina e não a fragmentos do DNA humano. Mais uma vez, somos confrontados com uma superinterpretação do resultado experimental. Quanto ao segundo elemento no qual a alegação CORVELVA se baseia, ou seja, que todo o genoma humano estaria presente nas vacinas, lembramos que nem é necessário ter acesso aos dados detalhados da cobertura para avaliar sua consistência: profundidade de seqüenciamento usada e com o número de leituras obtidas, essa afirmação é totalmente implausível. Além disso, a técnica de sequenciamento utilizada, baseada em sequências curtas, 125 nucleotídeos, não permite definir se um genoma está fragmentado. A técnica de sequenciamento usada apenas permite estimar a fração do DNA genômico sequenciado "
Resposta 7
O DNA humano nesta vacina é de aproximadamente 8 a 1 em relação ao DNA da varicela (88% das leituras são de origem humana, em comparação com 11% da catapora no último lote analisado A71CB256A). Outros vírus dsDNA atenuados não estão na vacina porque os vírus do sarampo, caxumba e rubéola são vírus de RNA de fita simples que não podem ser visualizados no gel de agarose. O NGS é uma tecnologia quantitativa, portanto, uma quantificação fluorimétrica simples do DNA total extraído da vacina (por exemplo, lote. A71CB256A = 3,7 microgramas por dose), associada à consideração da quantificação relativa feita acima (8: 1), nos permite ser capaz de dizer que o DNA celular é de cerca de 2,9 microgramas por dose, em comparação com cerca de 0.74 microgramas de DNA de varicela. Portanto, é plausível que pelo menos uma porção do DNA de alto peso molecular que é visto no gel possa ser a das células da linha celular fetal MRC5.
A evidência direta de que dentro deste produto existe um genoma humano COMPLETO (ou seja, com genes e seqüências não codificantes), fragmentada ou não, é fornecida pelo resultado do alinhamento das leituras derivadas de seres humanos na referência humana hg19.
A tabela a seguir, destacada em laranja, mostra o resultado expresso em 'Av_cov = cobertura média' do alinhamento das sequências humanas dos 3 lotes de Priorix testados (1º, 2º e 3º lote) em cromossomos humanos. Na coluna 1, chrM é o DNA mitocondrial, enquanto Chr1 a ChrY são os cromossomos humanos montados, incluindo os cromossomos sexuais X e Y. A coluna 2 mostra o comprimento dos cromossomos humanos montados expressos em pares de bases.
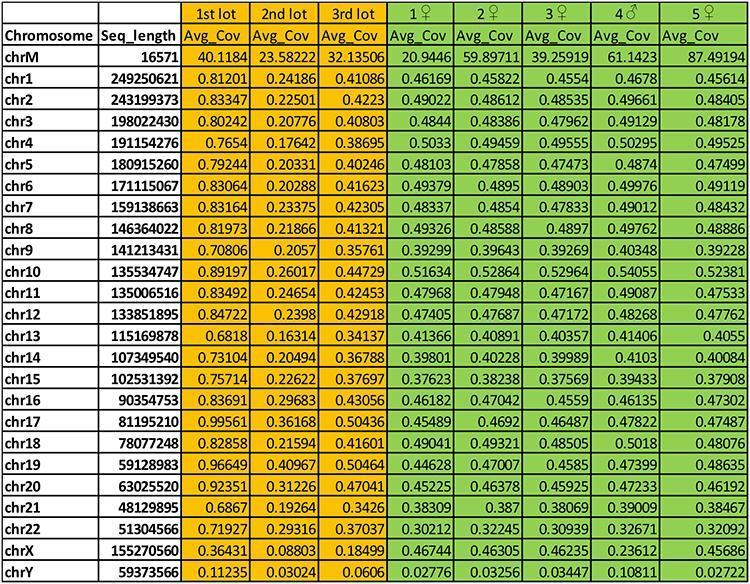
A cobertura é baixa (Avg_cov em média ao longo de cada cromossomo <que 1x), mas a homogeneidade de distribuição das leituras que se alinham exclusivamente, ao longo de todos os cromossomos humanos e a presença também de leituras que se alinham com maior cobertura no genoma mitocondrial (em células humanas há 2 genomas, um nuclear com cerca de 3Gbp grande e dividido em cromossomos e um menor, circular, com cerca de 16Kbp mitocondrial), no entanto, nos permite reconhecer inquestionavelmente uma situação semelhante ao sequenciamento do genoma passa-baixo de um genoma humano Individual. Para uma compreensão mais fácil do que é afirmado, na parte indicada em verde há algum sequenciamento de genoma inteiro passa-baixo humano (5 amostras, 4 mulheres e 1 homem) em uma profundidade semelhante à produzida para os 3 lotes de vacina de Priorix Tetra.
Uma indicação do sexo do indivíduo (provavelmente do sexo masculino) na vacina também pode ser deduzida da relação entre a cobertura média do cromossomo X e Y.
O DNA humano contido nos lotes previamente sequenciados de Priorix também foi qualificado como pertencente à linha fetal MRC-5, que é a linha celular contínua do tecido pulmonar de um feto abortivo masculino dos anos 60, no qual o vírus da varicela e rubéola. A análise das variantes do DNA mitocondrial presente na vacina em comparação com o DNA mitocondrial da linha MRC-5 (o DNA da linha celular foi comprado da ATCC, o principal recurso de materiais biológicos padrão no mundo) mostra que eles são o mesmo indivíduo.
Observação 8
"Há muito tempo evidências de que mesmo doses muito altas de DNA humano não podem induzir riscos significativos, mesmo durante longos períodos de observação, como confirmado por estudos sobre primatas não humanos, da experiência clínica com vacinas e outros medicamentos biológicos e de estudos recentes de avaliação de risco o que sugere que, mesmo nos países não europeus em que há limites para a quantidade de DNA injetável, esses limites são desnecessariamente rigorosos "
Resposta 8
O artigo de 1995 (https://www.sciencedirect.com/science/article/pii/S104510568570036X?via%3Dihub), citado por você, refere-se a um estudo sobre primatas, que, na minha opinião, certamente não é suficiente para demonstrar a ausência de infectividade, oncogenicidade e autoimunidade de DNA humano injetado em crianças, conforme declarado pelos mesmos autores na parte final da discussão. No experimento, uma grande quantidade de DNA humano é injetada em macacos, portanto, não é o DNA da mesma espécie.
O segundo artigo citado (https://www.ncbi.nlm.nih.gov/pubmed/23569076) afirma muito claramente que o DNA residual é infeccioso a 2 microgramas, mesmo que, em qualquer caso, esse limite seja obtido de uma avaliação estatística e não de dados experimentais. De qualquer forma, seguindo as indicações do autor, a vacina Priorix teria uma quantidade de DNA fetal claramente alinhada com a determinada em risco de doença infecciosa.
A Merck para a vacina Varivax (catapora, vírus vivo atenuado) declara no folheto americano a presença de DNA fetal humano derivado de células MRC-5 que, a partir das análises realizadas pelo Dr. Deisher, parece estar em uma quantidade de cerca de 2 microgramas.
No caso do folheto italiano do Priorix Tetra, no entanto, a presença de DNA da linha MRC-5 não é indicada, apesar de estar em quantidades da mesma ordem de magnitude que a contida no American Varivax. De qualquer forma, 2 microgramas de DNA fetal de MRC-5 não são, em minha opinião, uma quantidade residual, mas um componente real da vacina.
Os estudos in vitro do Dr. Deisher, que esperamos que sejam publicados em breve, infelizmente mostram resultados intrigantes quando uma vacina contendo DNA humano fetal (hipometilado) é incubada in vitro com células-tronco hematopoiéticas humanas. Mas esperamos que a pesquisa seja publicada e depois podemos nos encontrar novamente sobre o assunto.
Loretta Bolgan *
* Doutor em química e tecnologias farmacêuticas, com doutorado em ciências farmacêuticas pela Harvard Medical School Boston. Trabalhou no setor da indústria farmacêutica, onde trabalhou no registro e desenvolvimento de projetos de pesquisa na área de oncologia. A parte consultora da lei 210/92, poluição ambiental e doenças ocupacionais, participou da última comissão parlamentar de inquérito sobre urânio empobrecido no grupo de vacinas. Atual consultor da Ordem Nacional de Biólogos para a toxicologia de medicamentos e vacinas, ele também lida com nutrição e terapias complementares.
Download: CORVELVA-d.ssa-Loretta-Bolgan-encontrar-a-Bucci.pdf

