Génome humain Priorix Tetra et lignée cellulaire MRC-5 - étude comparative

Brève présentation des résultats
Aujourd'hui, nous présentons une étude approfondie et très importante sur le séquençage génomique de la lignée cellulaire que nous avons trouvée dans le vaccin quadrivalent MPRV (rougeole, rubéole, oreillons et varicelle) Priorix Tetra®, et celle de la lignée cellulaire MRC-5 ( celui qui aurait été utilisé dans le développement du vaccin lui-même).
Résumé des précédents rapports publiés:
- Premièrement, nous avons démontré que la quantité d'ADN présente dans le vaccin susmentionné est bien au-dessus du seuil autorisé;
- Deuxièmement, nous avons vérifié que la lignée cellulaire est bien le MRC-5 déclaré; 2
- Enfin, nous avons réalisé le séquençage du génome de la lignée cellulaire directement extrait du vaccin, mettant en évidence des mutations majeures qui ouvrent la possibilité de risques graves pour la santé lors de l'utilisation de ce vaccin.
Ce que nous présentons ici est précisément un travail comparatif entre les deux génomes: celui que nous avons trouvé à l'intérieur du vaccin et celui acheté à la banque de lignées cellulaires internationales sous le nom de MRC-5.
Le résultat est que les deux lignes présentent des différences importantes du point de vue de la stabilité génétique. En particulier, le génome du vaccin est significativement modifié par rapport à la lignée cellulaire enregistrée en 1966.
Cela signifie que les producteurs, dans ce cas de Priorix Tetra®, ont acheté la lignée cellulaire dans des conditions optimales du point de vue de la stabilité génétique et, par l'utilisation continue au fil du temps à des fins de production, ont commercialisé des vaccins contenant de plus en plus de matériel génétique humain modifié, dangereux pour la santé des vaccinés eux-mêmes.
Étant donné que les organismes de réglementation n'exigent pas de surveillance périodique de la stabilité génétique des lignées fœtales et ne fixent même pas de seuil minimal de sécurité, nous pouvons en déduire qu'une exigence fondamentale concernant la qualité et la sécurité des vaccins obtenus à partir de lignées cellulaires humaines n'a pas été respectée depuis un certain temps, à savoir la nécessité de vérifier qu'ils ne développent pas de mutations et de réarrangements potentiellement dangereux et d'assurer l'élimination des résidus de matériel génétique de transformation, le cas échéant.
Il n'est pas de notre responsabilité d'identifier quelle partie du processus de production ou de conservation pourrait affecter la qualité et la sécurité du produit, mais ce que nous pouvons confirmer aujourd'hui, en publiant ce rapport, c'est l'urgence de procéder à un examen approfondi des résultats de nos analyses. nous avons notifié ces deux dernières années, en nous concentrant sur le produit fini, vendu et administré et pas seulement sur les "ingrédients" uniques autorisés.
Nous tenons à rappeler une fois de plus que ces produits font partie du calendrier de vaccination italien et sont actuellement obligatoires pour la population pédiatrique dans notre pays ainsi que dans d'autres pays européens et en général à travers le monde.
Les organismes de réglementation ont une énorme responsabilité en matière de sécurité, qui est actuellement exprimée mais, dans la pratique, et pour autant que nos analyses le montrent, ne peut être garantie et n'est en fait clairement pas garantie.
Affichage circulaire des génomes (intrigue circulaire)
Une représentation graphique des deux génomes appelés «intrigue circos» est présentée ci-dessous.
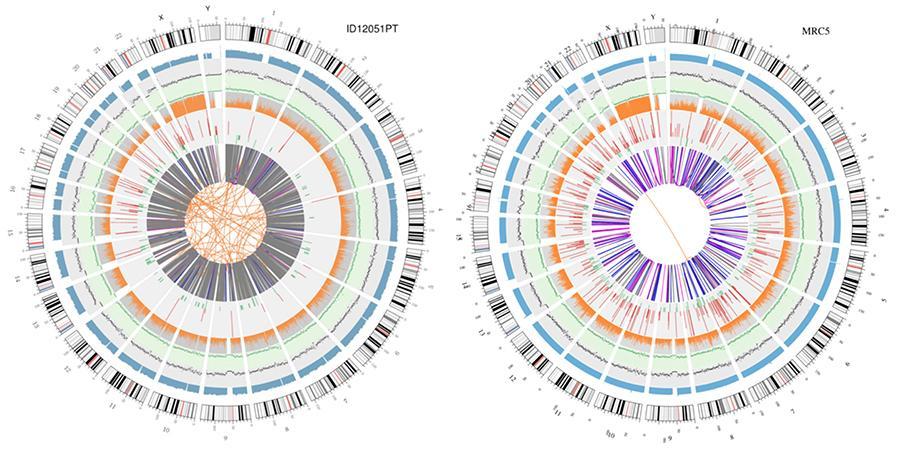
Explication des différents cercles concentriques
- Le cercle extérieur (le premier cercle) est le nombre de chromosomes.
- Le deuxième anneau (bleu) représente la couverture des lectures de style histogramme. Chaque histogramme est la couverture moyenne d'une zone de 0.5 Mbp.
- Le troisième anneau (noir) représente la densité des INDEL en style «graphique de dispersion». Chaque point noir est calculé comme le nombre d'INDEL (petites insertions / suppressions) dans une plage de 1 Mbp.
- Le quatrième anneau (vert) représente la densité snp dans le style «graphe de dispersion». Chaque point vert est calculé comme le nombre de SNP (variants de nucléotides uniques) dans une plage de 1 Mbp.
- Le cinquième anneau représente la proportion de SNP dans le style d'histogramme d'homozygotie (orange) et d'hétérozygotie (gris). Chaque histogramme est calculé à partir d'une région de 1 Mbp.
- Le sixième anneau représente l'inférence de CNV (Variantes en nombre de copies). Le rouge signifie le gain de morceaux d'ADN et le vert signifie la perte.
- L'anneau le plus central représente l'inférence des SV (variantes structurelles) dans les zones hexagonales et d'épissage. TRA (orange, translocations), INS (vert, insertions), DEL (suppressions, gris), DUP (duplications, rose) et INV (inversions, bleu).
Conclusion
Les deux génomes présentent des différences importantes. En particulier, le génome du vaccin apparaît gravement muté par rapport à la lignée cellulaire déposée en 1966. Il faut dire que nous n'avons pas eu la possibilité de séquencer la lignée cellulaire utilisée par GlaxoSmithKline pour la production du vaccin Priorix Tetra®, mais le l'un des stocks d'origine.
Les sociétés pharmaceutiques utilisant des lignées cellulaires pour la production de médicaments et de vaccins ont leur propre lignée MRC-5, mais ce fait ne change pas notre doute, c'est-à-dire qu'il n'y a pas de demande périodique de surveillance de la stabilité génétique, et c'est un problème majeur dans notre vue, en particulier parce que cela est autorisé sans limite de seuil.
Télécharger : CORVELVA-Priorix-Tetra-génome humain et MRC-5 cellules line.pdf
Génome humain Priorix Tetra® et lignée cellulaire MRC-5 - étude comparative (norme ATCC MRC-5 ATCC® CCL-171 ™)
La présence du virus de la rubéole a été démontrée en séquençant une bibliothèque d'ARN-seq avec une profondeur extrêmement élevée (environ 260 millions de séquences produites par Illumina). 114 séquences de 260 millions ont été détectées, soit 0.00004% du total des séquences. Les séquences du génome de la rubéole ont ensuite été confirmées manuellement avec le logiciel BLAST (Basic Local Alignment Search Tool, https://blast.ncbi.nlm.nih.gov/Blast.cgi). La bibliothèque séquencée à plus faible profondeur (environ 12 millions de séquences de correspondance Illumina, soit 6 millions de fragments de bibliothèque séquencés) n'avait détecté la présence d'aucune lecture attribuable à la rubéole, dans ce lot.
D'autres séquences virales présentes dans le vaccin (varicelle, rougeole et oreillons) ont également été validées de la même manière manuelle, confirmant qu'elles ont été correctement attribuées.
Introduction
Les séquenceurs de nouvelle génération sont devenus des outils de choix pour une analyse détaillée dans le domaine de la biologie et de la médecine, en particulier celui de précision. Ces outils permettent une approche nouvelle et plus globale d'une série d'applications telles que le séquençage de novo, la métagénomique, l'épigénomique, le séquençage du transcriptome et le reséquençage du génome.
Cette dernière application (re-séquençage) est répandue dans le domaine humain à la fois à des fins de recherche et de diagnostic et consiste en le séquençage avec la technologie NGS (Next Generation Sequencing) d'un génome individuel entier afin de cartographier des mutations nucléotidiques uniques (SNP, prononciation '' snip '), des insertions et des suppressions de séquences plus ou moins longues se sont produites dans certaines positions du génome et des variations du nombre de copies de portions de génome / gènes (CNV, Copy Number Variants).
La procédure de séquençage nécessite que l'ADN d'un individu soit mécaniquement divisé en fragments de petite taille (400-500 pb) et ces fragments sont liés à des tracts d'ADN artificiel appelés adaptateurs, qui permettent de fixer les fragments d'ADN humain sur une surface en verre sur lequel les bases sont ensuite lues (A, C, G, T).
La lecture de l'ADN est obtenue par incorporation de réactions chimiques de nucléotides marqués avec des molécules fluorescentes. Les millions de séquences (lectures) obtenues par séquençage se sont produites sur la surface en verre, sont ensuite cartographiées sur la référence du génome humain avec un logiciel approprié, puis toutes les variantes présentes dans le génome analysé par rapport à la référence sont identifiées.
Cette même procédure a été effectuée sur le génome humain présent dans le lot Priorix Tetra® n. A71CB256A et sur l'ADN extrait de la lignée cellulaire MRC-5, enregistré en 1966 à ATCC (MRC-5 ATCC® CCL-171 ™).
ATCC est la principale organisation mondiale de ressources et d'étalons de matériel biologique dont la mission se concentre sur l'acquisition, l'authentification, la production, la conservation, le développement et la distribution de micro-organismes de référence, de lignées cellulaires et d'autres matériaux biologiques standard. Il a été créé en 1925, lorsqu'un comité de scientifiques a reconnu la nécessité d'une collection centralisée de matériel biologique pouvant servir les scientifiques du monde entier.
La lignée cellulaire MRC-5 est dérivée du tissu pulmonaire normal d'un fœtus mâle âgé de 14 semaines et a été déposée à l'ATCC par JP Jacobs en septembre 1966. Ces cellules sont déclarées capables de doubler de 42 à 46 populations avant la sénescence. commence. L'article de référence pour cette lignée cellulaire remonte à 1970: https://www.nature.com/articles/227168a0
Résultats
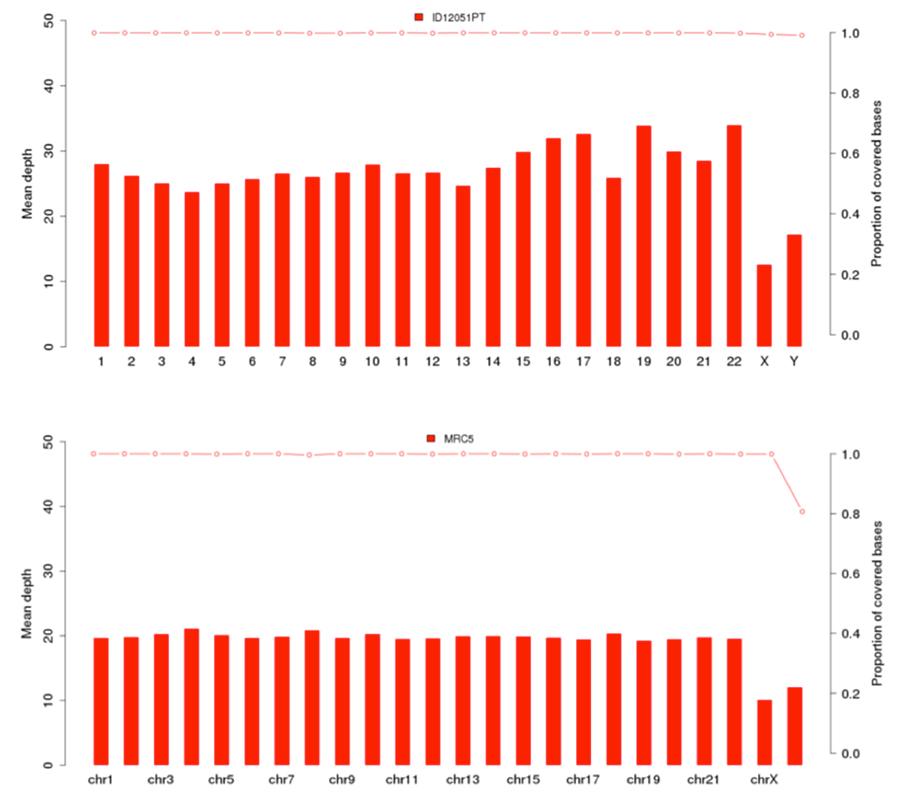
Comme indiqué précédemment, l'ADN humain présent dans le lot Priorix Tetra®. n. A71CB256A (indiqué dans les graphiques suivants comme "échantillon ID12051PT") est un génome individuel complet, c'est-à-dire que l'ADN génomique de tous les chromosomes d'un individu masculin est présent. Les graphiques de couverture (profondeur moyenne = couverture moyenne) des 22 chromosomes humains et des chromosomes X et Y sont présentés ci-dessous, pour le vaccin (image ci-dessus) et la lignée cellulaire MRC5 (image ci-dessous).
Ci-dessous sont présentés les résultats de l'analyse des différents types de variantes.
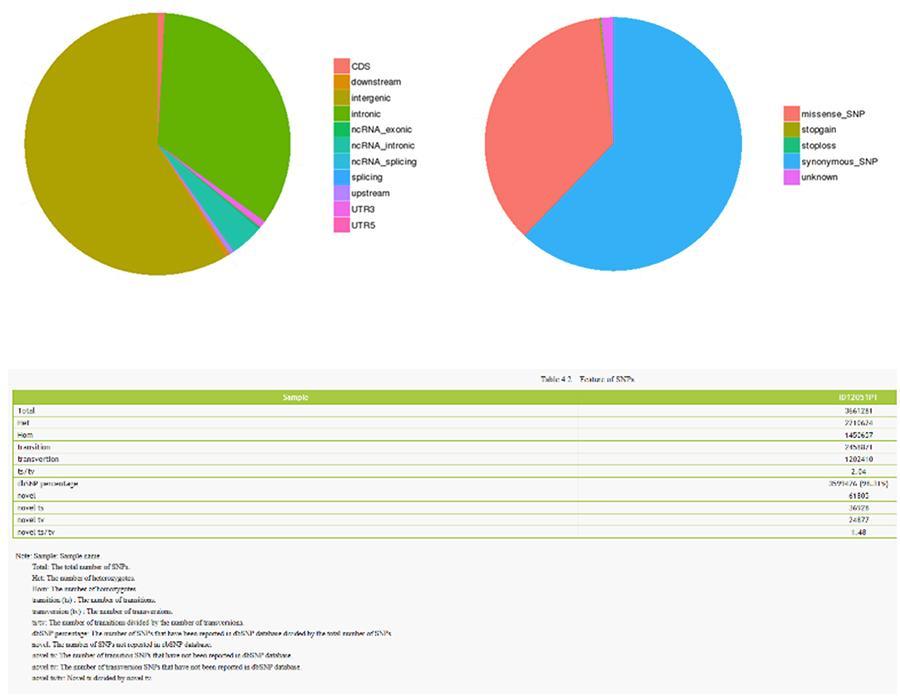
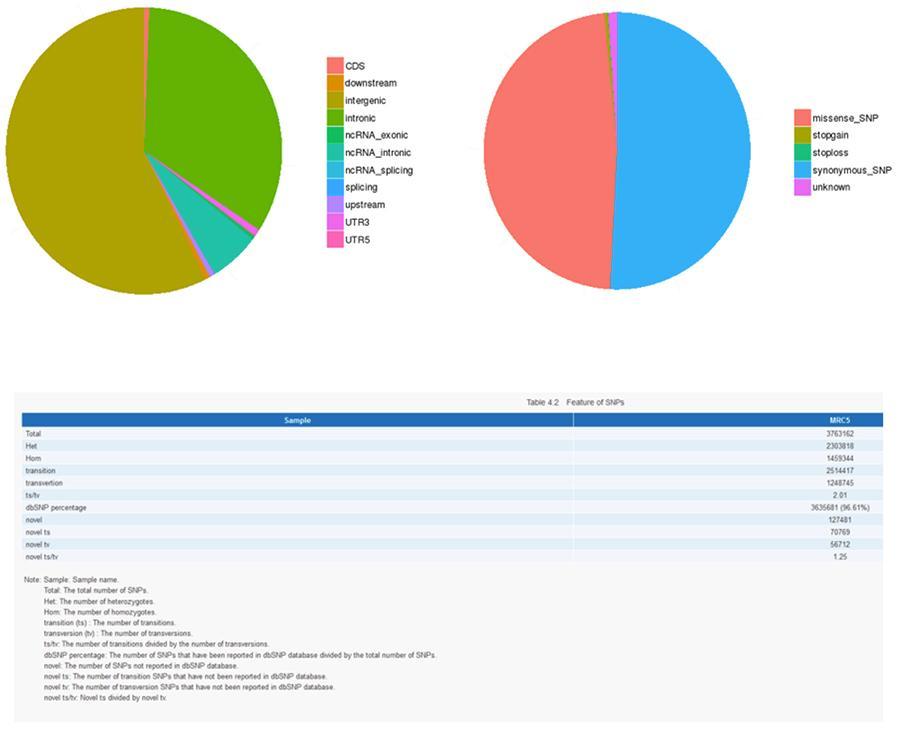
Polymorphisme mononucléotidique (SNP) et insertions / suppressions courtes (InDels)
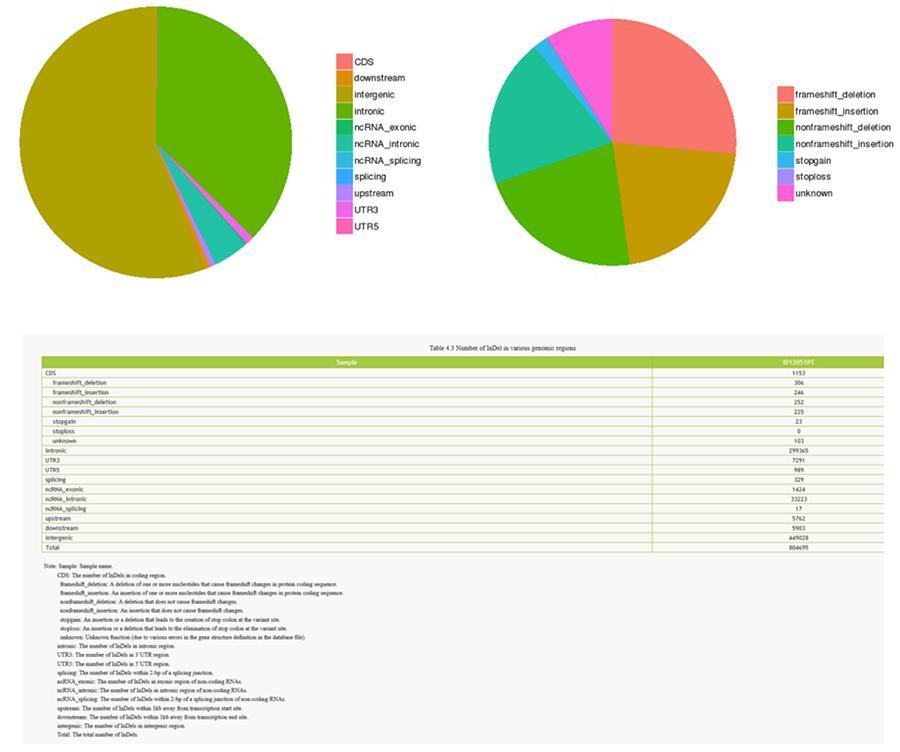
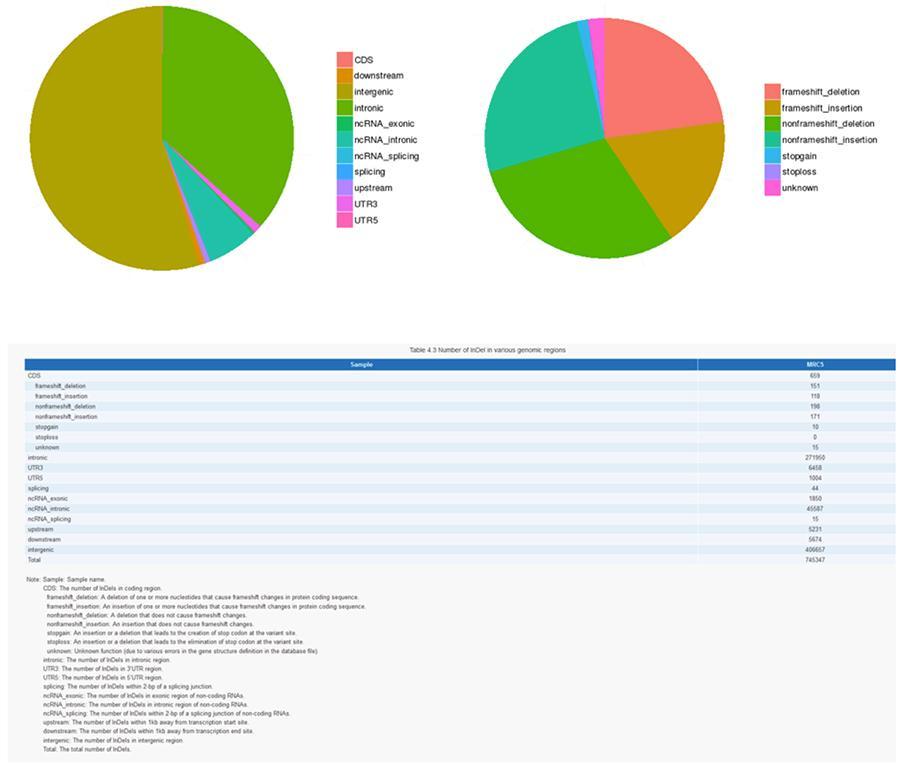
Les variantes d'un seul ADN individuel (SNP, prononcé «snip») sont des polymorphismes, c'est-à-dire des variations du matériel génétique, portées par un seul nucléotide. Les «InDels» sont de petites insertions et suppressions de moins de 50 pb de longueur et constituent une autre classe de variantes génomiques dans le génome humain.
SNP (polymorphisme mononucléotidique) - ID12051PT
SNP (polymorphisme mononucléotidique) - MRC-5
InDels (insertions / suppressions courtes) - ID12051PT
InDels (insertions / suppressions courtes) - MRC-5
CNV (Copy Number Variants) et SV (Structural Variants)
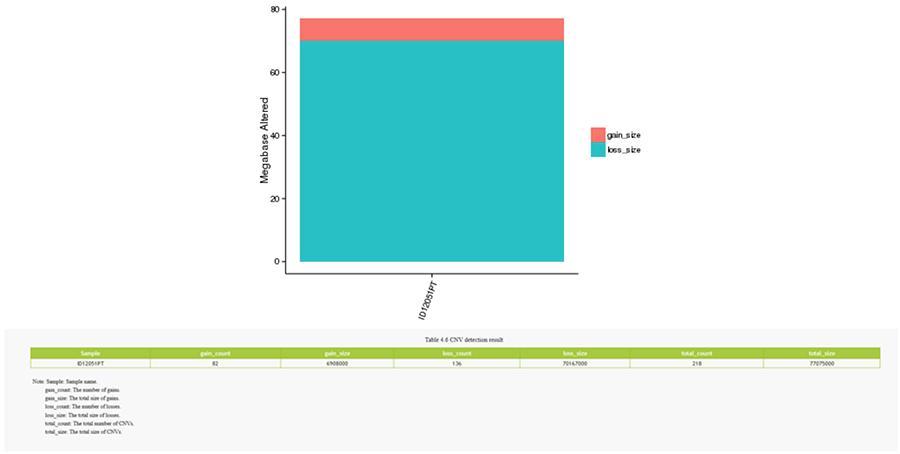
Les variantes du nombre de copies (CNV) sont des variantes génomiques en raison des variations du nombre de copies de fragments relativement gros (plus de 50 pb) dans les génomes individuels. Il existe deux types de CNV: le type «gain» (gain de copies) et le type «perte» (perte de copies).
Les variantes structurelles (SV) sont des variantes génomiques de dimensions relativement importantes (> 50 pb) comprenant des délétions, des duplications, des insertions, des inversions et des translocations.
CNV (variantes de numéro de copie)
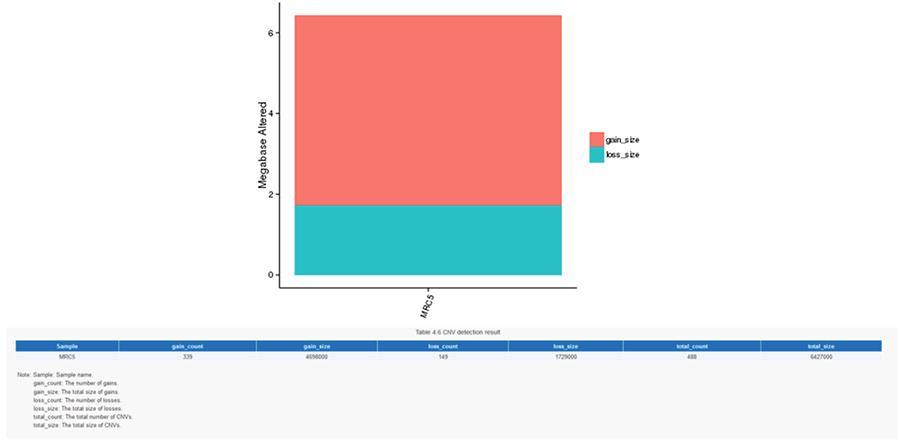
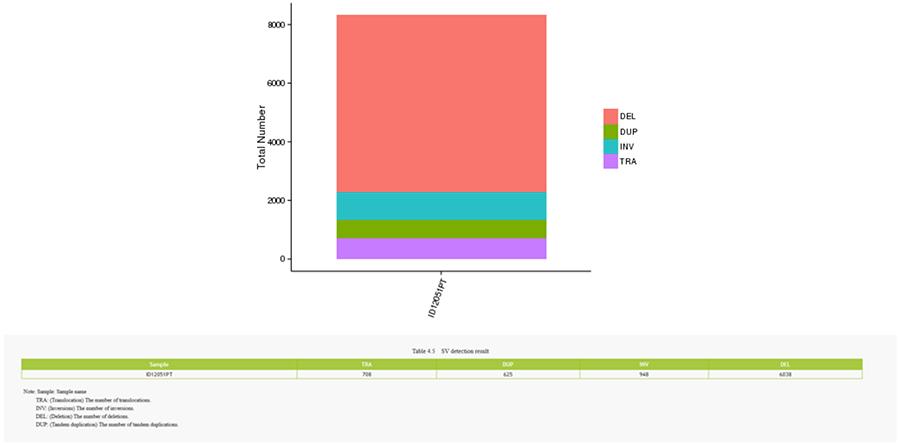
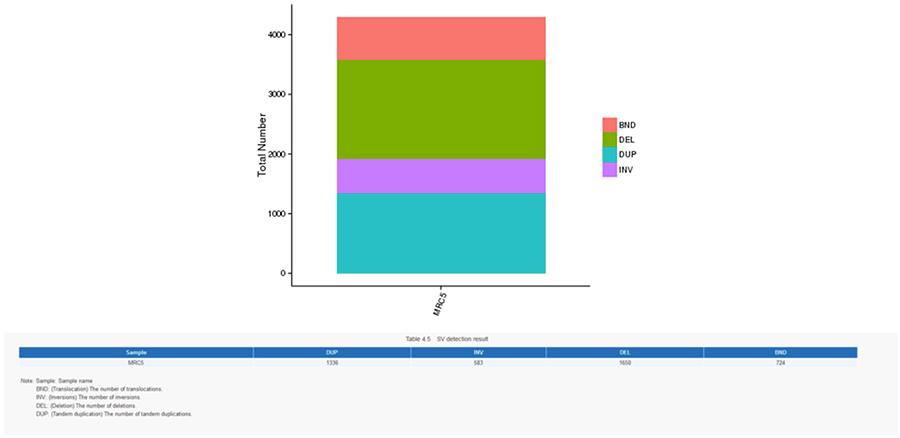
SV (variantes structurelles)
Visualisation circulaire des génomes (intrigue circulaire)
Une représentation graphique des deux génomes appelés (tracé circos) est présentée ci-dessous.
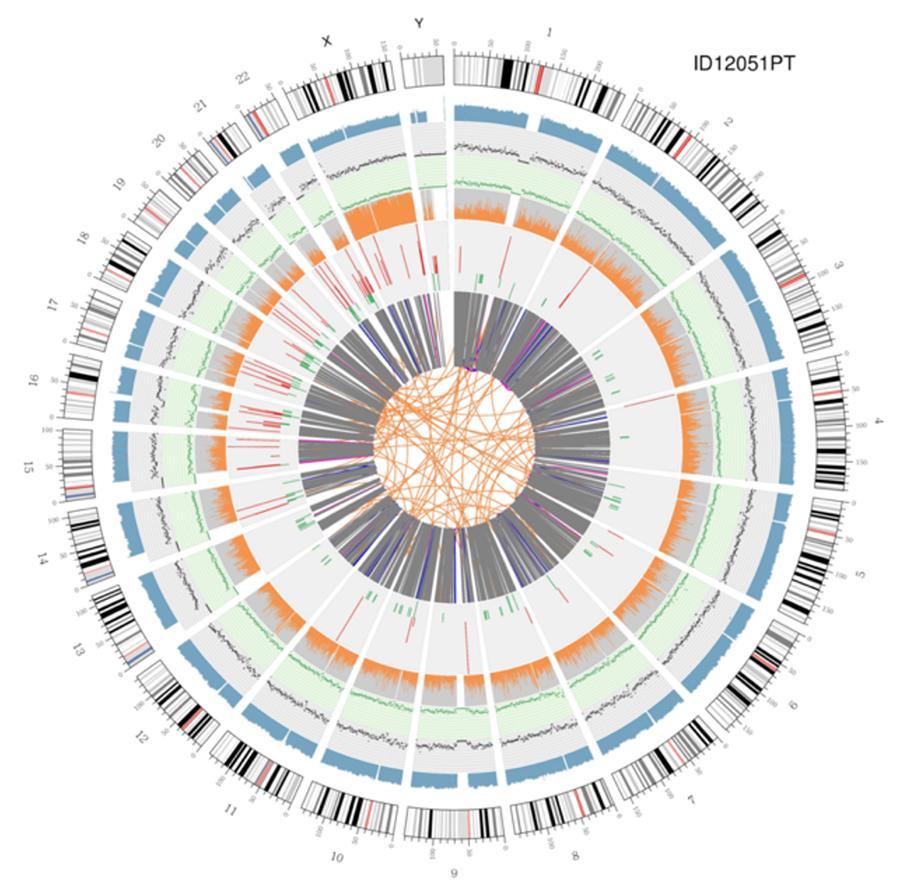
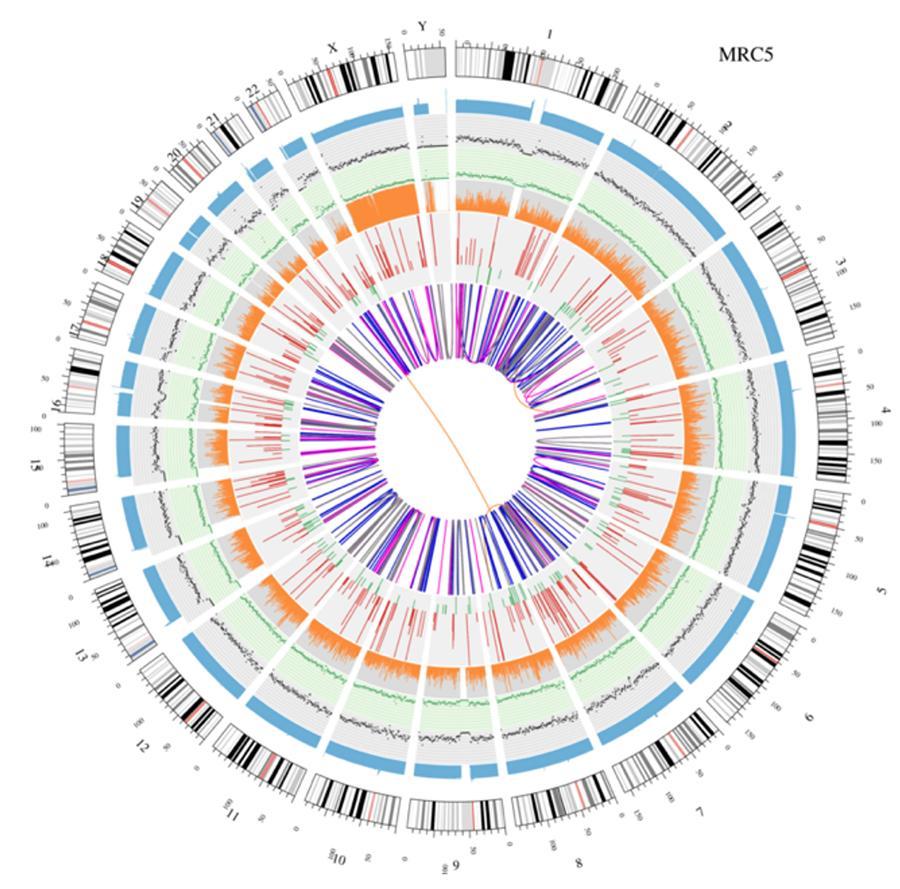
Signification des différents cercles concentriques
- Le cercle extérieur (premier cercle) est le numéro du chromosome.
- Le deuxième anneau (bleu) représente la couverture des lectures de type hystogramme. Chaque hystogramme est la couverture moyenne d'une zone de 0,5 Mbp.
- Le troisième anneau (noir) représente la densité des INDEL dans un «style de graphique de dispersion». Chaque point noir est calculé comme le nombre d'INDEL (petites insertions / suppressions) dans une plage de 1 Mbp.
- Le quatrième anneau (vert) représente la densité snp dans un «style de graphique de dispersion». Chaque point vert est calculé comme le nombre de SNP (polymorphismes mononucléotidiques) dans une plage de 1 Mbp.
- Le cinquième anneau représente la proportion de SNP homozygote (orange) et hétérozygote (gris) dans le style histogramme. Chaque histogramme est calculé à partir d'une région de 1 Mbp.
- Le sixième anneau représente l'inférence CNV (nombre de copies). Le rouge signifie que les morceaux d'ADN gagnent et le vert signifie la perte.
- L'anneau le plus central représente l'inférence SV (variantes structurales) dans les régions exoniques et d'épissage. TRA (translocation, orange), INS (insertions, vert), DEL (suppressions, gris), DUP (duplications, rose) et INV (inversions, bleu).
Conclusions
Ces deux génomes présentent des différences importantes. Plus précisément, le génome du vaccin se révèle être fortement modifié par rapport à celui de la lignée cellulaire déposée en 1966. Il faut dire que nous n'avons pas eu la possibilité d'effectuer le séquençage de la lignée cellulaire utilisée par GlaxoSmithKline pour la production de le vaccin Priorix Tetra®, mais celui du stock d'origine. Les sociétés pharmaceutiques qui utilisent des lignées cellulaires pour la production de médicaments et de vaccins ont leur propre lignée MRC-5, mais cela ne change pas nos soupçons, c'est-à-dire que le fait que le contrôle de la stabilité génétique n'est pas périodiquement nécessaire est très grave, à notre avis, surtout parce qu'il est permis d'être présent sans seuil limite.
Conclusions
Les deux génomes présentent des différences importantes. En particulier, le génome du vaccin se révèle fortement modifié par rapport à celui de la lignée cellulaire déposée en 1966. Il faut dire que nous n'avons pas eu la possibilité de séquencer la lignée cellulaire utilisée par GlaxoSmithKline pour la production du vaccin Priorix Tetra, mais celle du stock d'origine. Les sociétés pharmaceutiques qui utilisent des lignées cellulaires pour la production de médicaments et de vaccins ont leur lignée MRC-5 mais cela ne change pas nos soupçons, c'est le fait que le contrôle de la stabilité génétique n'est pas requis périodiquement et c'est très grave à notre avis , surtout parce qu'il est permis d'être présent sans limite.

