Genoma humano Priorix Tetra e linha celular MRC-5 - estudo comparativo

Breve apresentação dos resultados
Hoje, apresentamos um estudo aprofundado adicional e muito importante sobre o seqüenciamento genômico da linha celular que encontramos na vacina quadrivalente do MPRV (sarampo, rubéola, caxumba e varicela) Priorix Tetra® e na linha celular MRC-5 ( o declaradamente usado no desenvolvimento da vacina).
Resumindo relatórios publicados anteriormente:
- Primeiro, demonstramos que a quantidade de DNA presente na vacina mencionada acima está bem acima do limite permitido;
- Em segundo lugar, verificamos que a linha celular é realmente o MRC-5 declarado; 2
- Por fim, realizamos o sequenciamento do genoma da linha celular extraído diretamente da vacina, destacando as principais mutações que se abrem para a possibilidade de sérios riscos à saúde no uso dessa vacina.
O que estamos apresentando aqui é precisamente um trabalho comparativo entre os dois genomas: o que realmente encontramos na vacina e o adquirido no banco internacional de linha celular como MRC-5.
O resultado é que as duas linhas apresentam diferenças importantes do ponto de vista da estabilidade genética. Em particular, o genoma da vacina é significativamente modificado em comparação com a linha celular registrada em 1966.
Isso significa que os produtores, neste caso do Priorix Tetra®, adquiriram a linha celular em condições ideais do ponto de vista da estabilidade genética e, pelo uso contínuo e prolongado para fins de produção, comercializaram vacinas contendo progressivamente cada vez mais material genético humano modificado, perigoso para a saúde dos próprios vacinados.
Como as agências reguladoras não exigem monitoramento periódico da estabilidade genética das linhas fetais e nem mesmo estabelecem um limite mínimo de segurança, podemos deduzir que um requisito fundamental para a qualidade e segurança das vacinas obtidas de linhas celulares humanas não foi atendido. há algum tempo, a saber, a necessidade de verificar se não desenvolvem mutações e rearranjos potencialmente perigosos e garantir a eliminação do processamento de resíduos de material genético, se houver.
Não é nossa responsabilidade identificar qual parte do processo de produção ou preservação pode afetar a qualidade e a segurança do produto, mas o que podemos confirmar hoje, ao publicar este relatório, é a urgência de realizar um exame aprofundado dos resultados de nossas análises. temos notificado nos últimos dois anos, focando no produto acabado, vendido e administrado, e não apenas nos "ingredientes" autorizados.
Gostaríamos de lembrar mais uma vez que esses produtos fazem parte do cronograma de vacinação italiano e atualmente são obrigatórios para a população pediátrica em nosso país, bem como em outros países europeus e em geral em todo o mundo.
As agências reguladoras têm uma enorme responsabilidade com relação à segurança, que atualmente está sendo traduzida em palavras, mas, na prática, e até onde nossas análises mostram, não pode ser garantida e, de fato, claramente não é garantida.
Exibição circular de genomas (circos plot)
Uma representação gráfica dos dois genomas chamados 'circos plot' é mostrada abaixo.
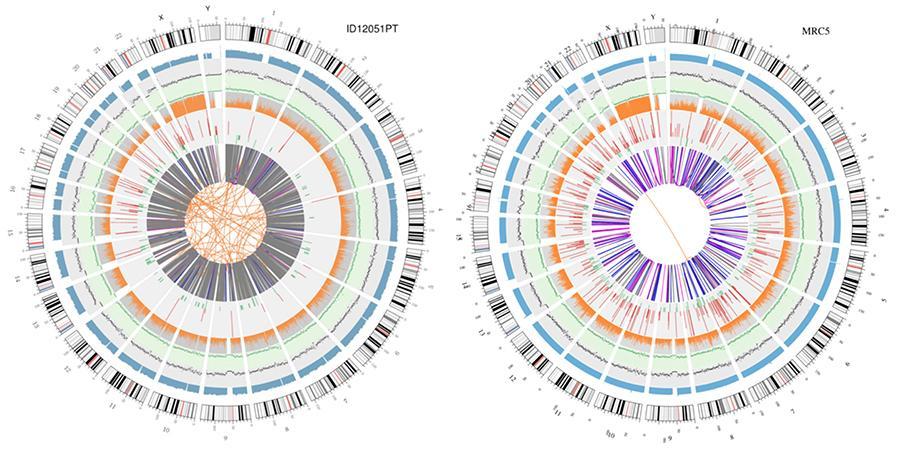
Explicação dos vários círculos concêntricos
- O círculo externo (o primeiro círculo) é o número do cromossomo.
- O segundo anel (azul) representa a cobertura das leituras do estilo do histograma. Cada histograma é a cobertura média de uma área de 0.5 Mbp.
- O terceiro anel (preto) representa a densidade dos INDELs no estilo 'gráfico de dispersão'. Cada ponto preto é calculado como o número de INDELs (pequenas inserções / exclusões) em uma faixa de 1 Mbp.
- O quarto anel (verde) representa a densidade snp no estilo 'gráfico de dispersão'. Cada ponto verde é calculado como o número de SNPs (variantes de nucleotídeo único) em uma faixa de 1 Mbp.
- O quinto anel representa a proporção de SNPs no estilo de histograma de homozigosidade (laranja) e heterozigosidade (cinza). Cada histograma é calculado a partir de uma região de 1 Mbp.
- O sexto anel representa a inferência de CNV (Variantes em número de cópias). Vermelho significa ganho de pedaços de DNA e verde significa perda.
- O anel mais central representa a inferência de SV (Variantes Estruturais) nas áreas hexagonal e de emenda. TRA (laranja, translocações), INS (verde, inserções), DEL (deleções, cinza), DUP (duplicações, rosa) e INV (inversões, azul).
Conclusão
Os dois genomas apresentam diferenças importantes. Em particular, o genoma da vacina parece estar seriamente mutado em comparação com a linhagem celular depositada em 1966. Deve-se dizer que não tivemos a possibilidade de sequenciar a linha celular usada pela GlaxoSmithKline para a produção da vacina Priorix Tetra®, mas a um do estoque original.
As empresas farmacêuticas que utilizam linhas celulares para a produção de medicamentos e vacinas possuem sua própria linha MRC-5, mas esse fato não altera nossa dúvida, ou seja, não há solicitação periódica de monitoramento da estabilidade genética, e esta é uma questão importante em nossa , especialmente porque isso é permitido sem um limite.
Download: CORVELVA-Priorix-Tetra-humano-genoma-e-MRC-5-célula-line.pdf
Genoma humano Priorix Tetra® e linha celular MRC-5 - estudo comparativo (padrão ATCC MRC-5 ATCC® CCL-171 ™)
A presença do vírus da rubéola foi demonstrada sequenciando uma biblioteca de RNA-seq com profundidade extremamente alta (aproximadamente 260 milhões de seqüências produzidas pela Illumina). Foram detectadas 114 seqüências de 260 milhões, igual a 0.00004% do total de seqüências. As sequências do genoma da rubéola foram então confirmadas manualmente com o software BLAST (Ferramenta básica de busca de alinhamento local, https://blast.ncbi.nlm.nih.gov/Blast.cgi). A biblioteca sequenciada em profundidade mais baixa (cerca de 12 milhões de seqüências de correspondência Illumina, igual a 6 milhões de fragmentos da biblioteca sequenciada) não havia detectado a presença de QUALQUER leitura atribuível à rubéola neste lote.
Outras seqüências de vírus presentes na vacina (varicela, sarampo e caxumba) também foram validadas da mesma maneira manual, confirmando que foram atribuídas corretamente.
Introdução
Os sequenciadores de nova geração tornaram-se ferramentas de escolha para análises detalhadas no campo da biologia e da medicina, especialmente o de precisão. Essas ferramentas permitem uma abordagem nova e mais global para uma série de aplicações como sequenciamento de novo, metagenômica, epigenômica, sequenciamento de transcriptoma e sequenciamento de genoma.
A última aplicação (re-sequenciamento) é difundida no campo humano, tanto para fins de pesquisa quanto para diagnóstico, e consiste no sequenciamento com a tecnologia NGS (Next Generation Sequencing) de um genoma individual inteiro para mapear mutações de nucleotídeo único (SNP, pronúncia '' snip '), inserções e deleções de sequências mais ou menos longas ocorreram em certas posições do genoma e variações no número de cópias de partes de genoma / genes (CNV, Copy Number Variants).
O procedimento de sequenciamento exige que o DNA de um indivíduo seja mecanicamente quebrado em fragmentos de tamanho pequeno (400-500 bp) e esses fragmentos estejam ligados a trechos de DNA artificial chamados adaptadores, que permitem fixar os fragmentos do DNA humano em uma superfície de vidro em que as bases são então lidas (A, C, G, T).
A leitura do DNA é obtida por meio da incorporação de reações químicas de nucleotídeos marcados com moléculas fluorescentes. Os milhões de sequências (leituras) que são obtidas por sequenciamento ocorridas na superfície do vidro são então mapeadas para a referência do genoma humano com software apropriado e, em seguida, todas as variantes presentes no genoma analisado em comparação com a referência são identificadas.
Este mesmo procedimento foi realizado no genoma humano presente no lote Priorix Tetra® n. A71CB256A e no DNA extraído da linha celular MRC-5, registrada em 1966 na ATCC (MRC-5 ATCC® CCL-171 ™).
A ATCC é a principal organização mundial de recursos e padrões de materiais biológicos cuja missão se concentra na aquisição, autenticação, produção, preservação, desenvolvimento e distribuição de microrganismos de referência, linhas celulares e outros materiais padrão biológicos. Foi criado em 1925, quando um comitê de cientistas reconheceu a necessidade de uma coleção centralizada de materiais biológicos que poderiam servir cientistas em todo o mundo.
A linha celular MRC-5 é derivada do tecido pulmonar normal de um feto masculino de 14 semanas e foi depositada no ATCC por JP Jacobs em setembro de 1966. Essas células são declaradas capazes de dobrar de 42 a 46 populações antes da senescência. começa. O artigo de referência para esta linha de células remonta a 1970: https://www.nature.com/articles/227168a0
Resultados
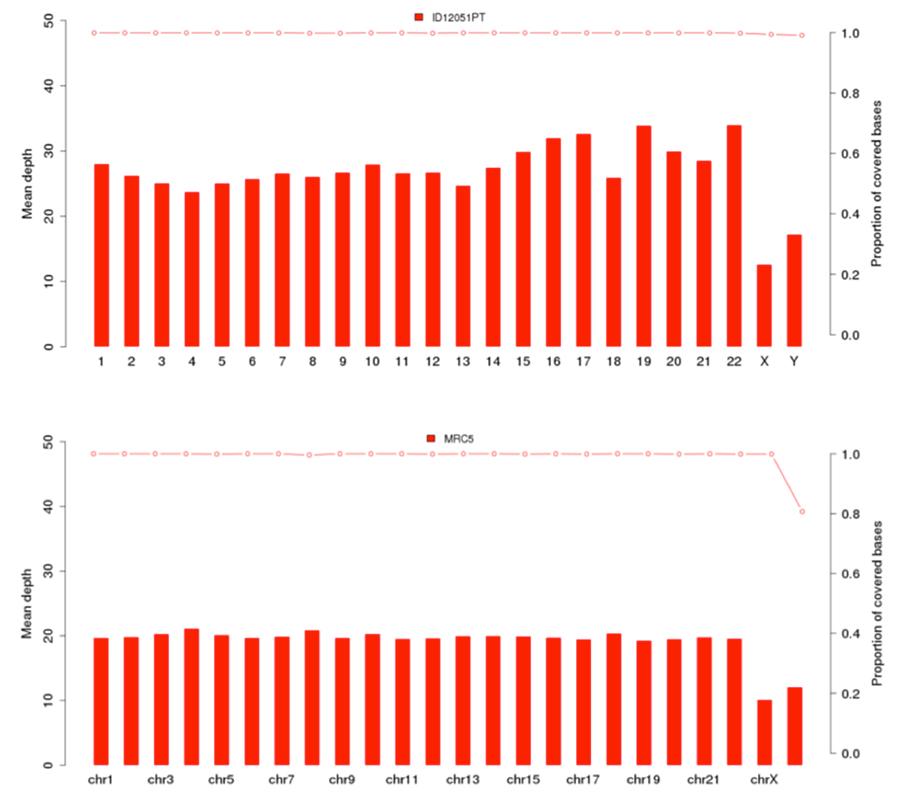
Como mostrado anteriormente, o DNA humano presente no lote Priorix Tetra®. n. A71CB256A (indicado nos gráficos a seguir como "amostra ID12051PT") é um genoma individual completo, ou seja, o DNA genômico de todos os cromossomos de um indivíduo do sexo masculino está presente. Os gráficos de cobertura (profundidade média = cobertura média) dos 22 cromossomos humanos e dos cromossomos X e Y são mostrados abaixo, para a vacina (imagem acima) e a linha celular MRC5 (imagem abaixo).
Abaixo são mostrados os resultados da análise dos vários tipos de variantes.
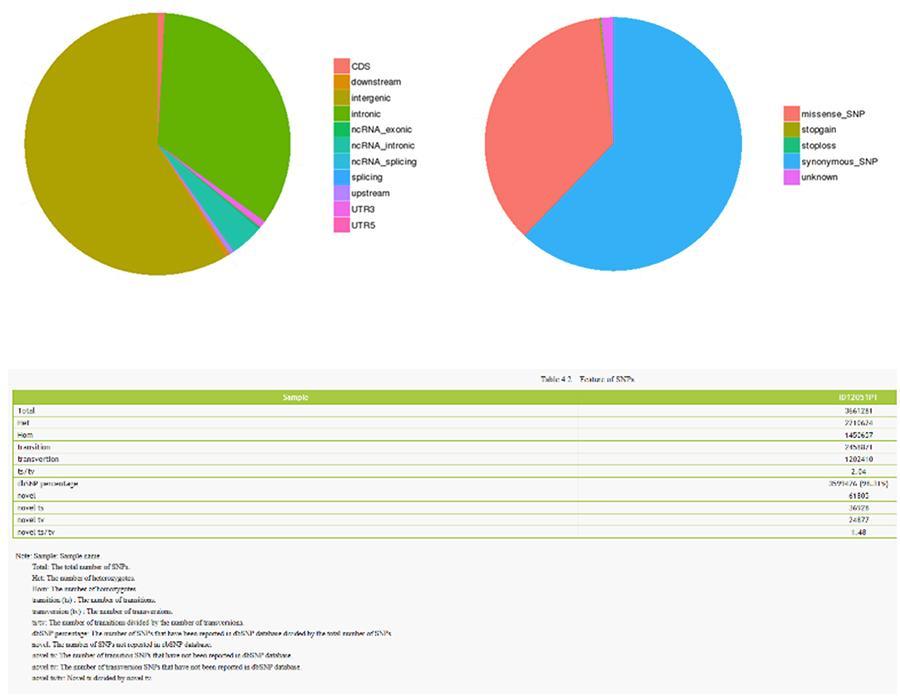
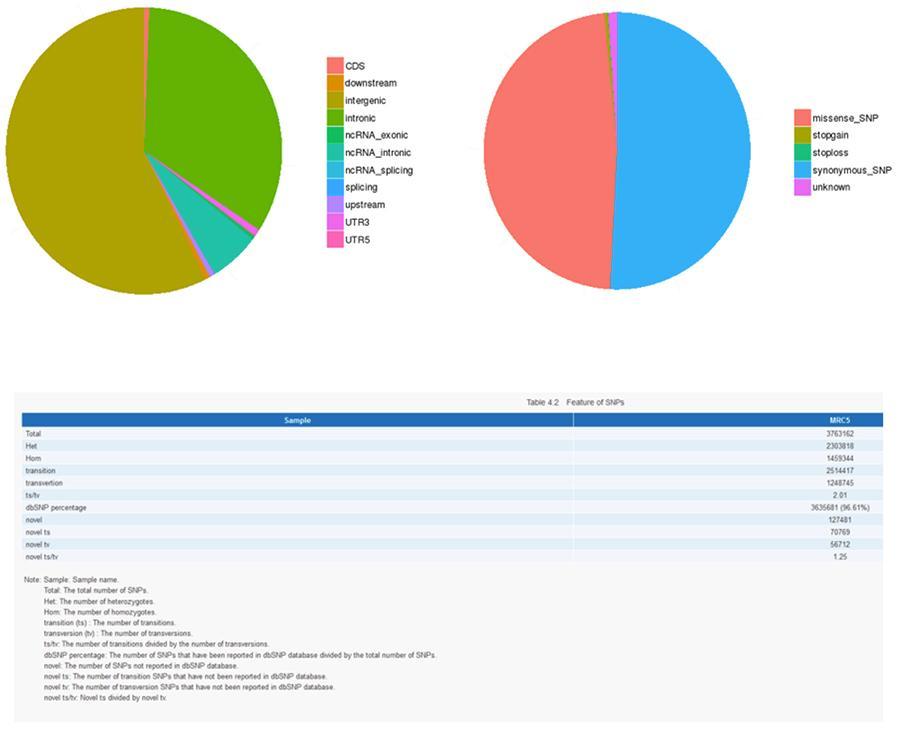
Polimorfismo de nucleotídeo único (SNP) e inserções / deleções curtas (InDels)
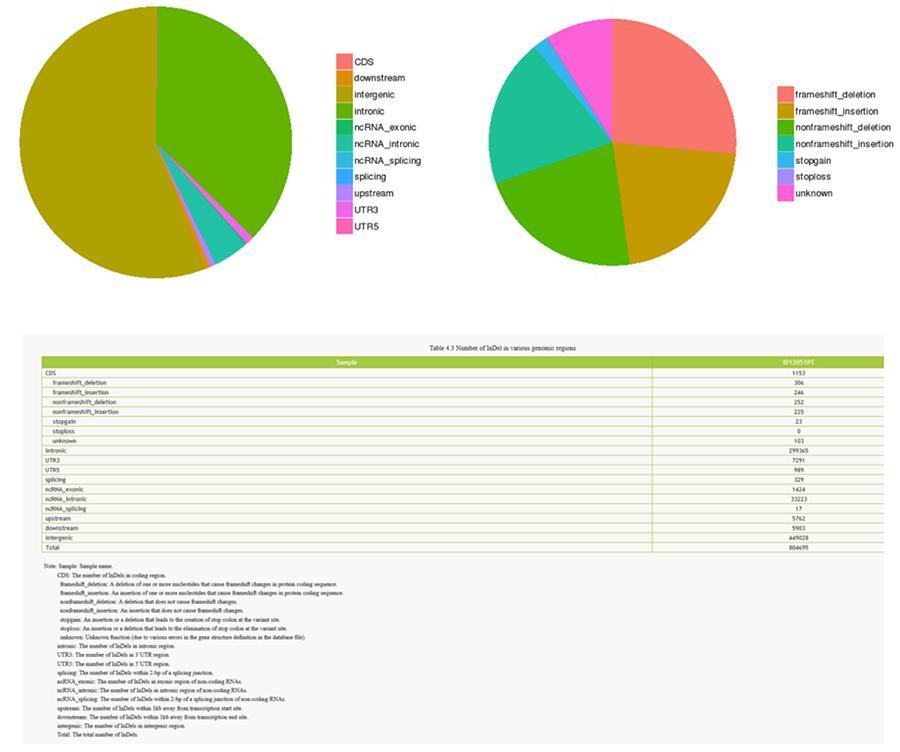
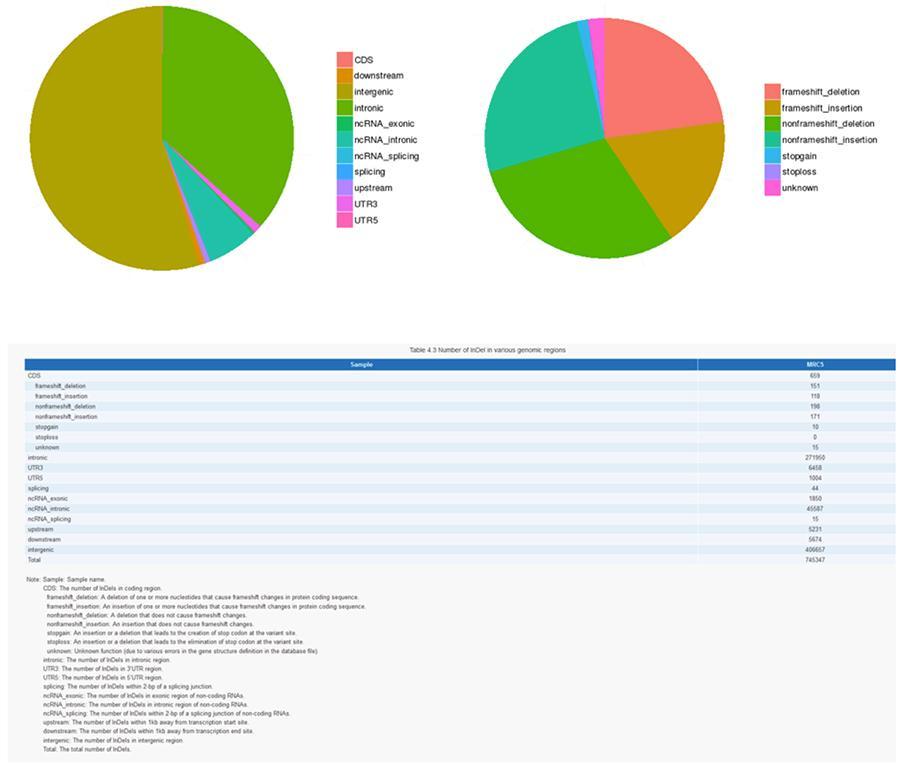
As variantes do DNA individual (SNP, pronunciado "snip") são polimorfismos, ou seja, variações do material genético, suportadas por um único nucleotídeo. Os 'InDels' são pequenas inserções e deleções com menos de 50 pb de comprimento e constituem outra classe de variantes genômicas no genoma humano.
SNP (polimorfismo de nucleotídeo único) - ID12051PT
SNP (polimorfismo de nucleotídeo único) - MRC-5
InDels (inserções / exclusões curtas) - ID12051PT
InDels (inserções / exclusões curtas) - MRC-5
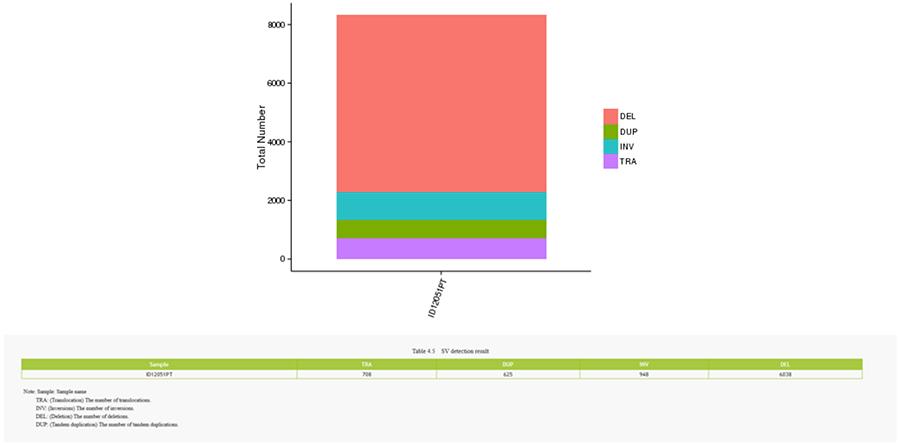
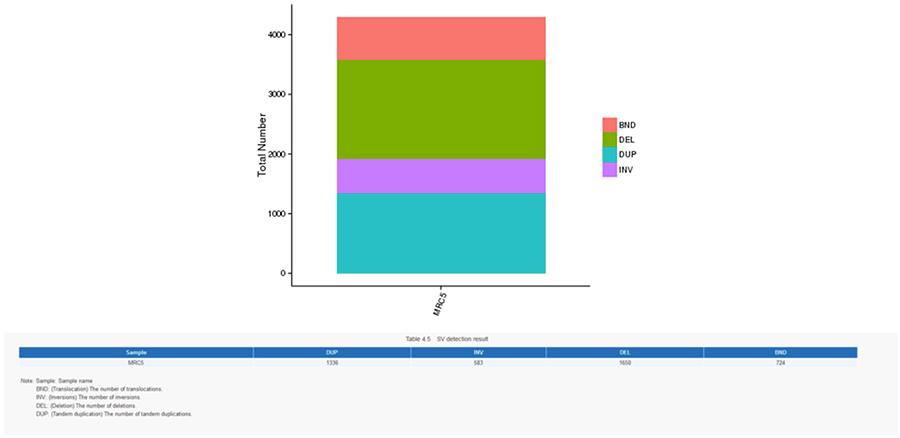
CNV (variantes do número de cópias) e SV (variantes estruturais)
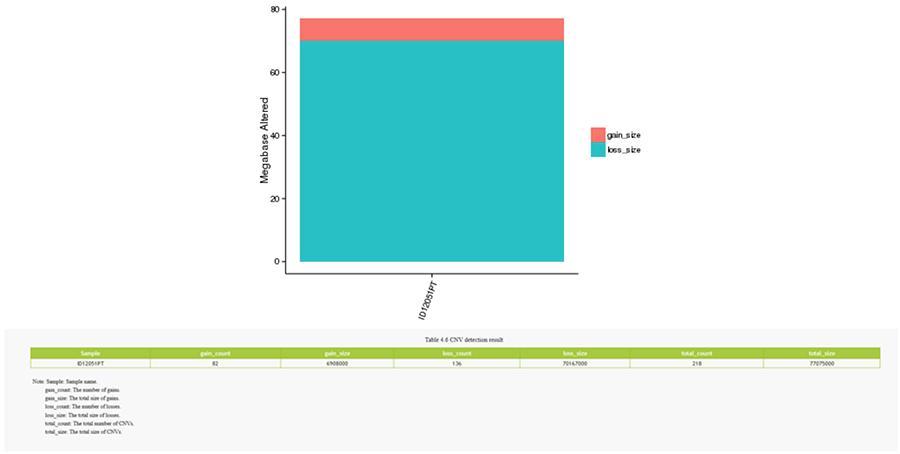
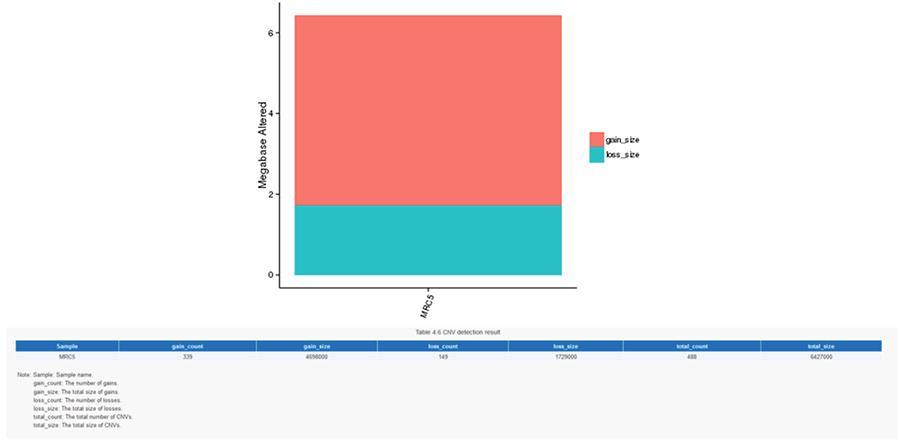
As variantes de número de cópias (CNV) são variantes genômicas devido a variações no número de cópias de fragmentos relativamente grandes (maiores que 50 pb) em genomas individuais. Existem dois tipos de CNV: tipo 'ganho' (ganho de cópias) e tipo 'perda' (perda de cópias).
Variantes estruturais (SV) são variantes genômicas com dimensões relativamente grandes (> 50 bp), incluindo deleções, duplicações, inserções, inversões e translocações.
CNV (variantes do número de cópias)
SV (variantes estruturais)
Visualização circular de genomas (circos plot)
Uma representação gráfica dos dois genomas chamados (plot circos) é mostrada abaixo.
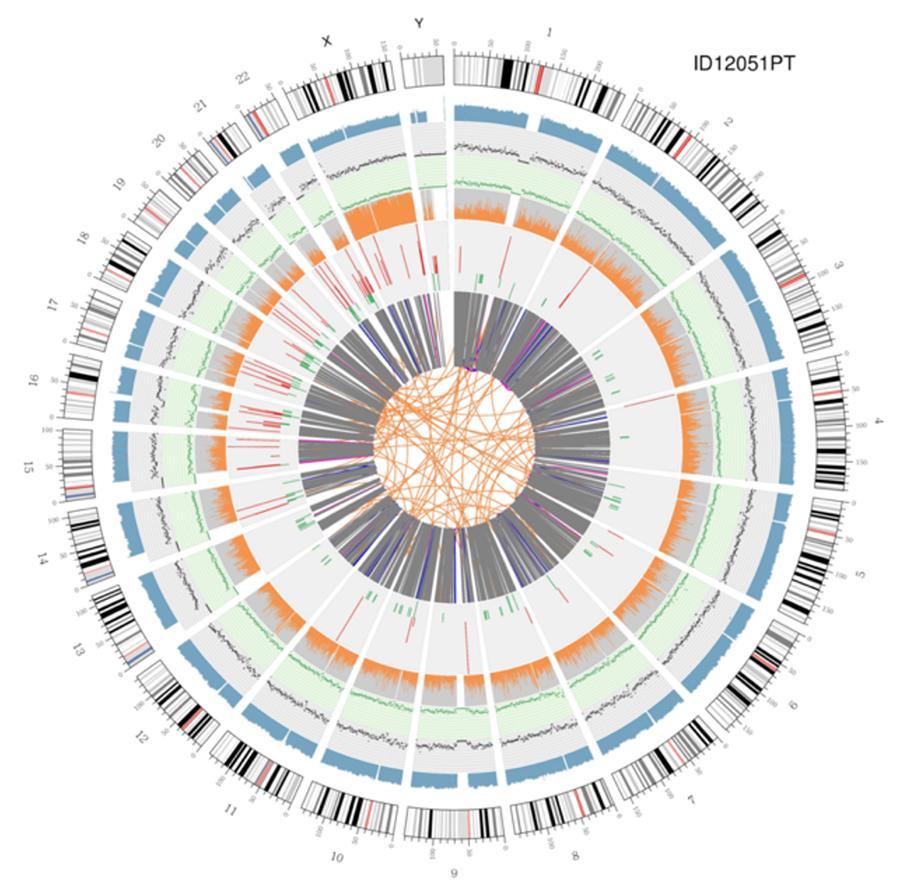
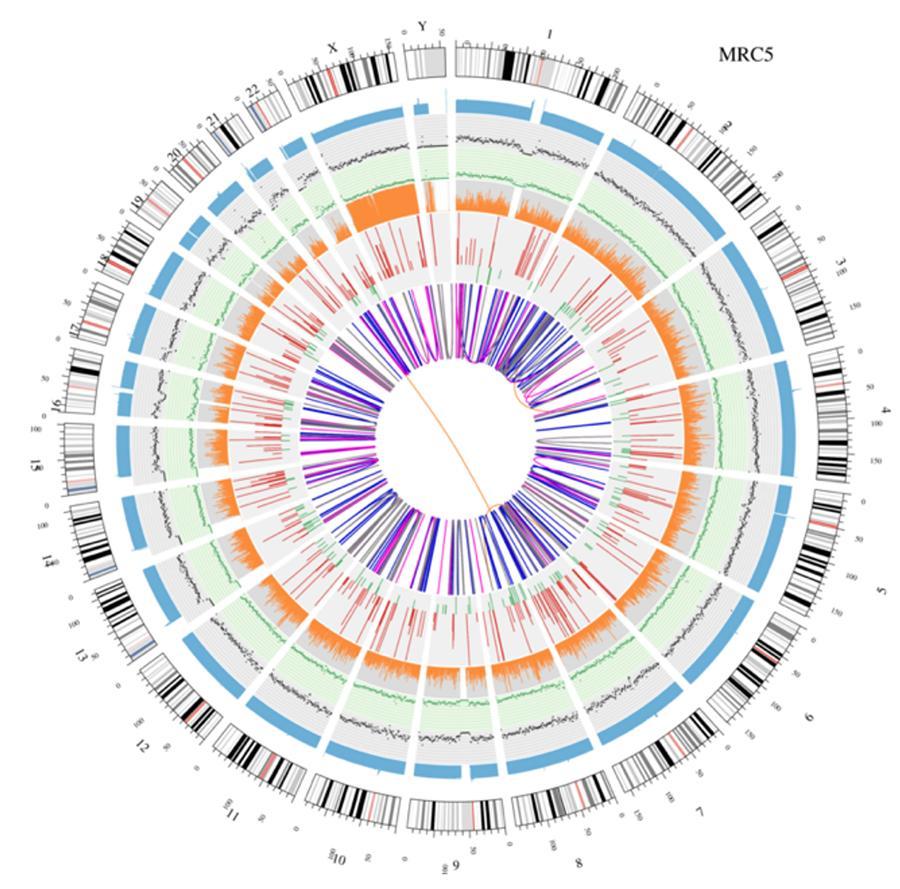
Significado dos vários círculos concêntricos
- O círculo externo (primeiro círculo) é o número do cromossomo.
- O segundo toque (azul) representa a cobertura das leituras no estilo do histograma. Cada histograma é a cobertura média de uma área de 0,5 Mbp.
- O terceiro anel (preto) representa a densidade dos INDELs em um 'estilo de gráfico de dispersão'. Cada ponto preto é calculado como o número de INDELs (pequenas inserções / exclusões) em um intervalo de 1 Mbp.
- O quarto anel (verde) representa a densidade snp em um 'estilo de gráfico de dispersão'. Cada ponto verde é calculado como o número de SNPs (polimorfismos de nucleotídeo único) na faixa de 1 Mbp.
- O quinto anel representa a proporção de SNP homozigoto (laranja) e heterozigoto (cinza) no estilo histograma. Cada histograma é calculado a partir de uma região de 1 Mbp.
- O sexto toque representa a inferência CNV (variantes do número de cópias). Vermelho significa ganho de peças de DNA e verde significa perda.
- O anel mais central representa a inferência SV (variantes estruturais) nas regiões exônicas e de união. TRA (translocação, laranja), INS (inserções, verde), DEL (exclusões, cinza), DUP (duplicações, rosa) e INV (inversões, azul).
Conclusões
Esses dois genomas mostram diferenças importantes. Especificamente, o genoma da vacina acaba sendo fortemente alterado em comparação ao da linhagem celular depositada em 1966. Pode-se dizer que não tivemos a possibilidade de realizar o seqüenciamento da linhagem celular usada pela GlaxoSmithKline para a produção de a vacina Priorix Tetra®, mas a do estoque original. As empresas farmacêuticas que usam linhas celulares para a produção de medicamentos e vacinas têm sua própria linha MRC-5, mas isso não muda nossas suspeitas, ou seja, o fato de que o controle da estabilidade genética não é necessário periodicamente é muito sério, em nossa opinião, especialmente porque é permitido estar presente sem limite de limite.
conclusões
Os dois genomas mostram diferenças importantes. Em particular, o genoma da vacina acaba sendo fortemente alterado em comparação com o da linhagem celular depositada em 1966. Deve-se dizer que não tivemos a possibilidade de sequenciar a linhagem usada pela GlaxoSmithKline para a produção da vacina Priorix Tetra, mas a do estoque originais. As empresas farmacêuticas que utilizam linhas celulares para a produção de medicamentos e vacinas têm sua linha MRC-5, mas isso não muda nossas suspeitas, ou seja, o fato de que o controle da estabilidade genética não é necessário periodicamente e isso é muito sério em nossa opinião. , acima de tudo, porque ele pode estar presente sem limite.

