Vaccinegate: MRC-5 contido no Priorix Tetra - Sequenciação completa do genoma

Essas análises mais recentes foram possíveis graças à contribuição ativa das associações francesas Associação Liberté Informações Santé (ALIS), Liga nacional para a libertação de vacinas (LNPLV) e a Associação Australiana Rede Australiana de Riscos de Vacinação (AVN), que agradecemos.
O sequenciamento de nova geração tornou-se a ferramenta preferida para análises aprofundadas no campo da biologia e da ciência médica, especialmente as de alta precisão. Graças a essas ferramentas, podemos abordar de uma forma mais moderna e abrangente uma série de aplicações, como sequenciamento de novo, estudos metagenômicos e epigenômicos, sequenciamento de transcriptoma e re-sequenciamento de genoma.
Este último (re-sequenciamento) é amplamente utilizado no campo humano, tanto para fins de pesquisa e diagnóstico e consiste em NGS - Sequenciamento de próxima geração de um único genoma inteiro, para mapear as mutações de nucleotídeo único (SNP), inserções e deleções de mais ou sequências menos longas que ocorreram em certas localizações do genoma e variações no número de cópias de porções / genes genômicos (CNV, Copy Number Variants).
Este procedimento ajuda a entender o mecanismo de desenvolvimento de algumas patologias, a fim de identificar as direções para um futuro tratamento clínico, como no caso do câncer, por exemplo. De fato, por esse método, a herança genética de um paciente com câncer pode ser totalmente decodificada em tecidos normais e cancerígenos, permitindo assim compreender o que exatamente mudou no genoma e, se possível, como intervir com medidas direcionadas.
O procedimento de re-sequenciamento requer que o DNA de um indivíduo seja mecanicamente quebrado em fragmentos de pequena dimensão (400-500 pares de bases) e partes artificiais de DNA denominadas adaptadores sejam ligadas a esses fragmentos; adaptadores permitem ligar os fragmentos de DNA humano a uma superfície de vidro na qual é realizada a leitura de bases (A, C, G, T). A leitura dos pares de bases do DNA ocorre por meio de reações químicas, nomeadamente a incorporação de nucleotídeos marcados por moléculas fluorescentes. Os milhões de sequências (leituras) assim obtidas são então mapeadas no genoma de referência humano por software específico e todas as variantes são identificadas comparando o genoma analisado com o genoma de referência.
Este mesmo procedimento foi realizado no genoma humano no Priorix® Tetra lote n. A71CB256A, genoma que pertence à linha celular MRC-5 (de origem fetal); o trabalho é realizado por uma empresa dos EUA que trabalha rotineiramente com análise de sequenciamento do genoma humano. *
* o nome do laboratório que realizou a análise será incluído na próxima reclamação formal que apresentaremos ao Ministério Público de Roma e também aos órgãos reguladores italianos e europeus. As associações que estão apresentando a análise financiada pela Corvelva também serão prontamente atualizadas com esses resultados chocantes. Não podemos negar que nos sentimos, especialmente como pais, angustiados com os resultados que estamos relatando - como se o que descobrimos até agora não fosse suficiente para nos preocupar.
Resultados
Verificou-se que o genoma de referência humano corresponde a 99.76% das leituras do DNA da vacina, o que significa quase toda a sua totalidade. O DNA fetal humano apresentado nesta vacina é um único genoma inteiro, o que significa que a vacina contém DNA genômico com todos os cromossomos de um indivíduo do sexo masculino (de fato, o MRC-5 se origina de um feto masculino).
A seguir, são apresentados os resultados da análise de diferentes tipos de variantes em comparação com o genoma humano de referência.
Variante de nucleotídeo único (SNP - polimorfismo de nucleotídeo único) e inserções / deleções curtas (InDels)
As variantes de bases únicas do DNA (SNP) são polimorfismos, o que significa mutações no material genético de um único nucleotídeo.
Os 'InDels' são, em vez disso, pequenas inserções e deleções com comprimento inferior a 50 pb e constituem uma classe diferente de variantes genômicas no genoma humano.
No genoma humano da vacina, 3.6 milhões de SNP foram identificados (98.31% dos quais já foram relatados no banco de dados público dbSNP e 61.805 novos, o que significa original neste DNA) e cerca de 804.000 InDels (89.42% dos quais já relatados no dbSNP e 85.106 novo).
A quantidade de SNP está de acordo com o que foi relatado na literatura sobre / no "genoma humano típico", enquanto o InDels resulta em uma quantidade maior em comparação com o que foi relatado pelo "The 1000 Genomes Project Consortium", ou seja, 800.000 em comparação com 600.000 .
CNV (variantes do número de cópias) e SV (variantes estruturais)
As variantes do número de cópias (CNVs) são variantes genômicas devido a variações no número de cópias de fragmentos relativamente grandes (maiores que 50 pb) entre genomas individuais. Existem dois tipos de CNVs: tipo "ganho" (ganho de cópias) e tipo "perda" (perda de cópias). 218 CNVs foram detectados no genoma da vacinação humana, dos quais 82 foram "ganhos" (cobrindo uma parte do genoma de cerca de 6.9 milhões de pares de bases) e 136 CNVs do tipo "perda" (cobrindo uma porção do genoma de cerca de 70 milhões de bases).
Conforme descrito pelo The 1000 Genomes Project Consortium em "Uma referência global para variação genética humana (Nature, vol. 526, 10 de outubro de 2015)", um genoma humano típico contém de 2,100 a 2,500 grandes variantes, incluindo:
- 1,000 exclusões grandes
- 160 variantes no número de cópias (CNVs)
- 10 inversões
Que juntos afetam os 20 milhões de bases da sequência, considerando também as inserções.
Como observado para os INDELs curtos, mesmo no caso de grandes inserções e deleções, o genoma da vacina não está, portanto, alinhado com um genoma humano "normal", sendo muito mais "reorganizado" do que o genoma de uma pessoa comum.
Visão circular do genoma (circos plot)
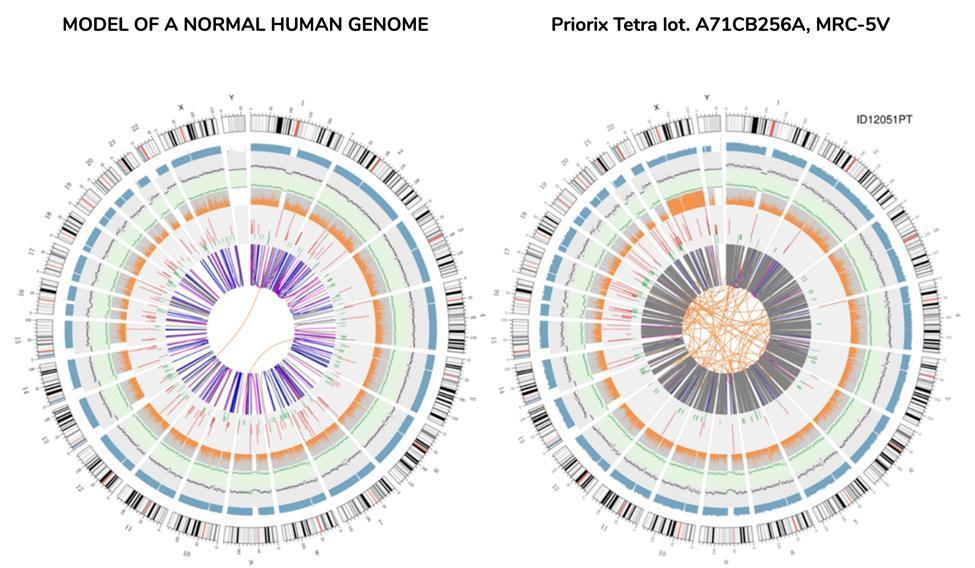
Uma representação gráfica do genoma da vacina chamada "circos plot" (comumente usada para representar um genoma re-sequenciado) é mostrada abaixo, ao lado de outra representando um genoma re-sequenciado a partir do DNA extraído do sangue de um indivíduo saudável - genoma "normal" :
Significado dos círculos concêntricos
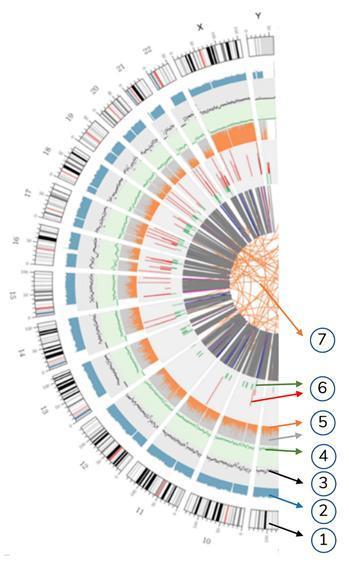
7) O anel mais central representa a inferência SV (Variantes Estruturais) nas regiões de éxons e de emenda. TRA (laranja, translocações), INS (verde, inserções), DEL (deleções, cinza), DUP (duplicações, rosa) e INV (inversões, azul).
6) o sexto círculo representa a inferência CNV (variantes do número de cópias). Vermelho significa ganho de seqüências de DNA e verde significa perda.
5) O quinto anel representa a proporção de SNP em homozigose (laranja) e heterozigose (cinza) no layout do histograma.
4) O quarto anel (verde) representa a densidade do SNP no layout do gráfico de dispersão.
3) O terceiro toque (preto) representa a densidade do INDEL no layout do gráfico de dispersão.
2) O segundo toque (azul claro) representa a cobertura das leituras no layout do histograma.
1) O círculo externo (o primeiro círculo) é o número do cromossomo.
Uma comparação aproximada também pode ser feita entre o DNA fetal e o DNA das células HeLa, a linha celular imortalizada usada também para produzir a vacina contra a poliomielite.
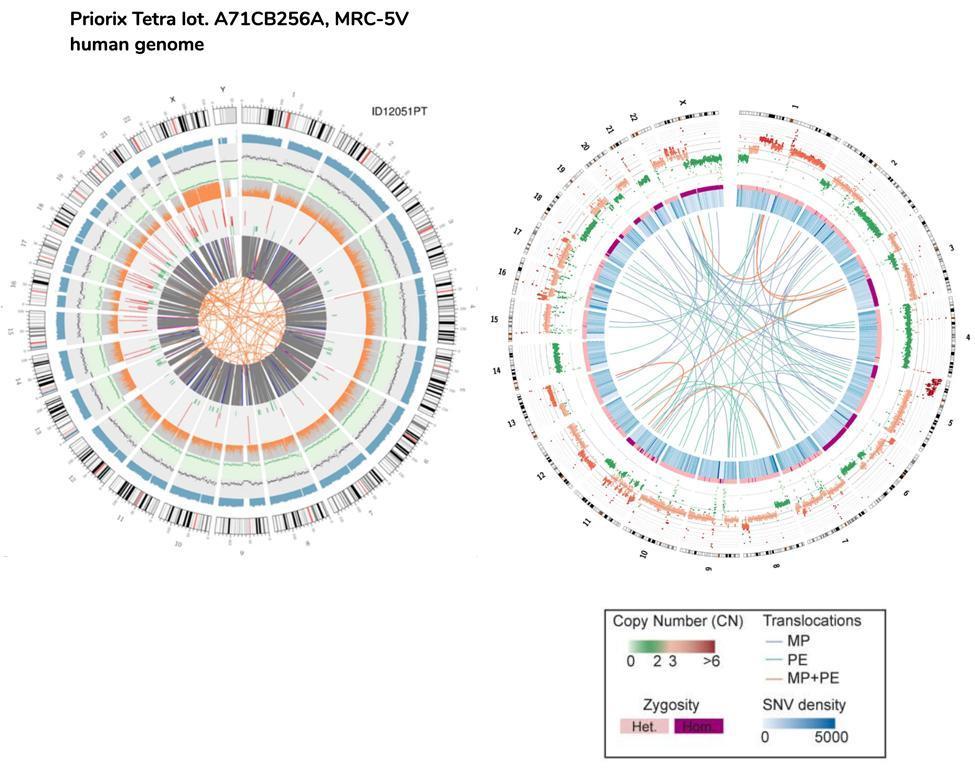
Observe que as translocações das células HeLa representadas no gráfico de circos pelas linhas do núcleo são referidas a todo o genoma (daí a parte codificadora e não codificadora), enquanto que no caso das células de vacinação fetal, elas se referem apenas aos genes codificadores .
Não é preciso ser um cientista para entender dos circos, simplesmente à primeira vista, que o genoma da vacina não é um genoma que pode ser definido como "normal". As linhas laranja entrelaçadas no centro dos circos, não tão numerosas no anel correspondente do genoma "normal", já fazem sentido para a anomalia desse genoma.
Análise de variantes em genes de câncer
A análise das variantes SNP, InDels, CNV, SV em 560 genes escolhidos por se envolverem em diferentes formas de câncer humano mostra a presença de inúmeras variantes "originais", ou seja, elas nem sequer estão presentes em bancos de dados públicos; desconhecido na literatura. Em outras palavras, importantes modificações de genes que se sabe estarem associadas a várias formas de tumor foram identificadas para todos os 560 genes verificados; além disso, existem variantes cujas conseqüências não são conhecidas, mas que, no entanto, afetam os genes envolvidos na indução do câncer humano.
Conclusão
O DNA genômico humano contido na vacina lote Priorix. n. O A71CB256A é evidentemente anômalo, apresentando inconsistências importantes se comparado a um genoma humano típico, isto é, o de um ser humano saudável. Existem várias variantes desconhecidas (não registradas em bancos de dados públicos) e algumas delas estão localizadas em genes envolvidos no câncer. O que também é aparentemente anômalo, é o excesso de genoma que mostra alterações no número de cópias (CNV) e variantes estruturais (SV), como translocações, inserções, deleções, duplicações e inversões, muitas das quais envolvem genes.
A contribuição potencial das inúmeras variantes (não presentes na literatura científica e nas bases de dados públicas) para o fenótipo das células utilizadas para o crescimento de vírus vacinais é desconhecida.
Dentro do PDF, você encontrará todas as informações relacionadas também às implicações para a saudação e a correspondência com a EMA.
Download: CORVELVA-MRC-5-contido-em-Priorix-Tetra-Completa-genoma-sequenciação

