Priorix Tetra Humangenom und MRC-5-Zelllinie - Vergleichsstudie

Kurze Präsentation der Ergebnisse
Heute präsentieren wir eine weitere und sehr wichtige eingehende Studie zur genomischen Sequenzierung der Zelllinie, die wir im vierwertigen MPRV-Impfstoff (Masern, Röteln, Mumps und Windpocken) Priorix Tetra® und der MRC-5-Zelllinie ( diejenige, die angeblich bei der Entwicklung des Impfstoffs selbst verwendet wurde).
Zusammenfassung früherer veröffentlichter Berichte:
- Zunächst haben wir gezeigt, dass die im oben genannten Impfstoff vorhandene DNA-Menge deutlich über dem zulässigen Schwellenwert liegt.
- Zweitens haben wir überprüft, dass die Zelllinie tatsächlich das deklarierte MRC-5 ist; 2
- Zuletzt führten wir die Sequenzierung des direkt aus dem Impfstoff extrahierten Zellliniengenoms durch, wobei wir wichtige Mutationen hervorhoben, die die Möglichkeit schwerwiegender Gesundheitsrisiken bei der Verwendung dieses Impfstoffs eröffnen.
Was wir hier präsentieren, ist genau eine Vergleichsarbeit zwischen den beiden Genomen: dem, das wir tatsächlich im Impfstoff gefunden haben, und dem, das von der internationalen Zelllinienbank als MRC-5 gekauft wurde.
Das Ergebnis ist, dass die beiden Linien unter dem Gesichtspunkt der genetischen Stabilität wichtige Unterschiede aufweisen. Insbesondere das Impfstoffgenom ist im Vergleich zu der 1966 registrierten Zelllinie signifikant verändert.
Dies bedeutet, dass die Hersteller, in diesem Fall von Priorix Tetra®, die Zelllinie unter optimalen Bedingungen unter dem Gesichtspunkt der genetischen Stabilität gekauft und durch die im Laufe der Zeit kontinuierliche Verwendung für Produktionszwecke Impfstoffe vermarktet haben, die zunehmend mehr enthalten modifiziertes menschliches genetisches Material, das für die Gesundheit der Impfstoffe selbst gefährlich ist.
Da die Aufsichtsbehörden keine regelmäßige Überwachung der genetischen Stabilität fetaler Linien verlangen und nicht einmal eine Mindestsicherheitsschwelle festlegen, können wir daraus schließen, dass eine grundlegende Anforderung an die Qualität und Sicherheit von Impfstoffen aus menschlichen Zelllinien nicht erfüllt wurde einige Zeit, nämlich die Notwendigkeit, zu überprüfen, ob sie keine potenziell gefährlichen Mutationen und Umlagerungen entwickeln, und die Beseitigung der Verarbeitung von genetischen Materialresten sicherzustellen, falls vorhanden.
Es liegt nicht in unserer Verantwortung zu ermitteln, welcher Teil des Produktions- oder Konservierungsprozesses die Produktqualität und -sicherheit beeinträchtigen könnte. Was wir heute durch die Veröffentlichung dieses Berichts bestätigen können, ist die Dringlichkeit, eine eingehende Prüfung unserer Analyseergebnisse durchzuführen. Wir haben in den letzten zwei Jahren benachrichtigt und uns auf das fertige Produkt konzentriert, das verkauft und verwaltet wird, und nicht nur auf die einzelnen zugelassenen "Zutaten".
Wir möchten noch einmal daran erinnern, dass diese Produkte Teil des italienischen Impfplans sind und derzeit für die pädiatrische Bevölkerung in unserem Land sowie in anderen europäischen Ländern und allgemein auf der ganzen Welt vorgeschrieben sind.
Die Aufsichtsbehörden haben eine große Verantwortung in Bezug auf die Sicherheit, die derzeit in Worte gefasst wird, aber in der Praxis und soweit unsere Analysen zeigen, nicht garantiert werden kann und tatsächlich eindeutig nicht garantiert wird.
Zirkuläre Darstellung von Genomen (Circos Plot)
Eine grafische Darstellung der beiden Genome, die als "Circos Plot" bezeichnet wird, ist unten dargestellt.
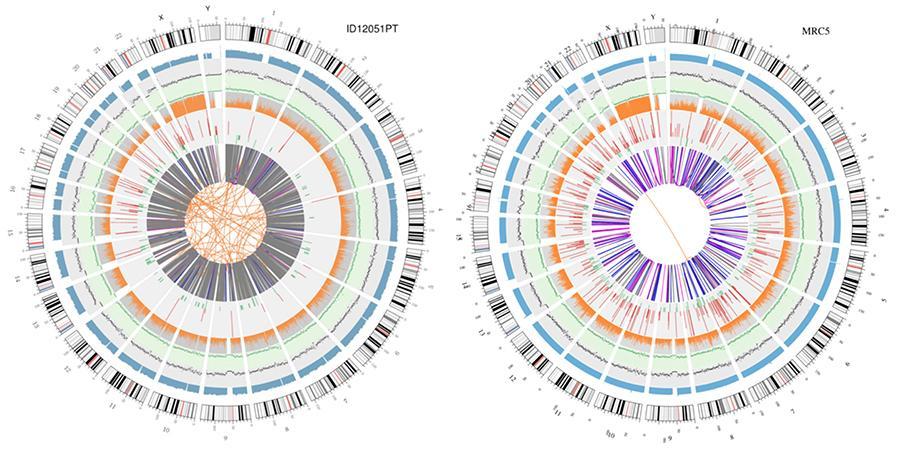
Erklärung der verschiedenen konzentrischen Kreise
- Der äußere Kreis (der erste Kreis) ist die Chromosomenzahl.
- Der zweite Ring (blau) repräsentiert die Abdeckung der Lesevorgänge im Histogrammstil. Jedes Histogramm ist die durchschnittliche Abdeckung einer Fläche von 0.5 Mbit / s.
- Der dritte Ring (schwarz) repräsentiert die Dichte der INDELs im Dispersionsgraphenstil. Jeder schwarze Punkt wird als Anzahl der INDELs (kleine Einfügungen / Löschungen) in einem Bereich von 1 Mbit / s berechnet.
- Der vierte Ring (grün) repräsentiert die snp-Dichte im Dispersionsgraphenstil. Jeder grüne Punkt wird als Anzahl von SNPs (Einzelnukleotidvarianten) in einem Bereich von 1 Mbit / s berechnet.
- Der fünfte Ring repräsentiert den Anteil der SNPs im Histogrammstil Homozygotie (orange) und Heterozygotie (grau). Jedes Histogramm wird aus einer 1-Mbit / s-Region berechnet.
- Der sechste Ring repräsentiert die Inferenz von CNV (Varianten in Anzahl der Kopien). Rot bedeutet Gewinn an DNA-Stücken und Grün bedeutet Verlust.
- Der zentralste Ring repräsentiert die Inferenz von SV (Strukturvarianten) im hexagonalen und Spleißbereich. TRA (orange, Translokationen), INS (grün, Insertionen), DEL (Deletionen, grau), DUP (Duplikationen, pink) und INV (Inversionen, blau).
Zusammenfassung
Die beiden Genome weisen wichtige Unterschiede auf. Insbesondere scheint das Impfstoffgenom im Vergleich zu der 1966 hinterlegten Zelllinie ernsthaft mutiert zu sein. Es muss gesagt werden, dass wir nicht die Möglichkeit hatten, die von GlaxoSmithKline für die Herstellung des Priorix Tetra®-Impfstoffs verwendete Zelllinie zu sequenzieren, sondern die einer der ursprünglichen Lager.
Pharmaunternehmen, die Zelllinien zur Herstellung von Arzneimitteln und Impfstoffen verwenden, haben ihre eigene MRC-5-Linie, aber diese Tatsache ändert nichts an unserem Zweifel, das heißt, es gibt keine regelmäßige Anforderung zur Überwachung der genetischen Stabilität, und dies ist ein Hauptproblem in unserer Ansicht, insbesondere weil dies ohne Schwellenwert zulässig ist.
Herunterladen: CORVELVA-Priorix-Tetra-Human-Genom-and-MRC-5-Zellen-line.pdf
Priorix Tetra® Humangenom und MRC-5-Zelllinie - Vergleichsstudie (ATCC-Standard MRC-5 ATCC® CCL-171 ™)
Das Vorhandensein des Rötelnvirus wurde durch Sequenzierung einer RNA-seq-Bibliothek mit extrem hoher Tiefe (ungefähr 260 Millionen von Illumina produzierte Sequenzen) nachgewiesen. Es wurden 114 Sequenzen von 260 Millionen nachgewiesen, was 0.00004% der Gesamtsequenzen entspricht. Die Rötelngenomsequenzen wurden dann manuell mit der BLAST-Software (Basic Local Alignment Search Tool, https://blast.ncbi.nlm.nih.gov/Blast.cgi). Die in geringerer Tiefe sequenzierte Bibliothek (etwa 12 Millionen Übereinstimmungssequenzen Illumina, entsprechend 6 Millionen Fragmente der sequenzierten Bibliothek) hatte in dieser Charge keine ANY-Reads festgestellt, die auf Röteln zurückzuführen waren.
Andere im Impfstoff vorhandene Virussequenzen (Windpocken, Masern und Mumps) wurden ebenfalls auf die gleiche manuelle Weise validiert, um zu bestätigen, dass sie korrekt zugeordnet wurden.
Einleitung
Die Sequenzer der neuen Generation sind zu Werkzeugen der Wahl für detaillierte Analysen auf dem Gebiet der Biologie und Medizin geworden, insbesondere im Bereich der Präzision. Diese Tools ermöglichen einen neuen und globaleren Ansatz für eine Reihe von Anwendungen wie De-novo-Sequenzierung, Metagenomik, Epigenomik, Transkriptomsequenzierung und Genom-Re-Sequenzierung.
Die letztere Anwendung (Re-Sequenzierung) ist sowohl für Forschungs- als auch für diagnostische Zwecke im menschlichen Bereich weit verbreitet und besteht in der Sequenzierung eines gesamten individuellen Genoms mit der NGS-Technologie (Next Generation Sequencing), um einzelne Nukleotidmutationen (SNP, Aussprache) abzubilden. snip '), Insertionen und Deletionen von mehr oder weniger langen Sequenzen traten an bestimmten Positionen des Genoms und Variationen in der Anzahl der Kopien von Teilen des Genoms / der Gene (CNV, Copy Number Variants) auf.
Das Sequenzierungsverfahren erfordert, dass die DNA eines Individuums mechanisch in Fragmente kleiner Größe (400-500 bp) zerbrochen wird und diese Fragmente mit künstlichen DNA-Trakten verbunden sind, die als Adapter bezeichnet werden und die es ermöglichen, die Fragmente menschlicher DNA auf einer Glasoberfläche zu fixieren auf denen dann die Basen gelesen werden (A, C, G, T).
Die DNA-Ablesung wird durch Einbau chemischer Reaktionen von mit fluoreszierenden Molekülen markierten Nukleotiden erhalten. Die Millionen von Sequenzen (Reads), die durch Sequenzierung auf der Glasoberfläche erhalten werden, werden dann mit geeigneter Software auf die Referenz des menschlichen Genoms abgebildet, und dann werden alle im analysierten Genom vorhandenen Varianten im Vergleich zur Referenz identifiziert.
Das gleiche Verfahren wurde an dem in Priorix Tetra® Charge n vorhandenen menschlichen Genom durchgeführt. A71CB256A und auf der DNA, die aus der MRC-5-Zelllinie extrahiert wurde und 1966 bei ATCC registriert wurde (MRC-5 ATCC® CCL-171 ™).
ATCC ist die weltweit führende Organisation von Ressourcen und Standards für biologisches Material, deren Mission sich auf den Erwerb, die Authentifizierung, die Produktion, die Konservierung, die Entwicklung und den Vertrieb von Referenzmikroorganismen, Zelllinien und anderen biologischen Standardmaterialien konzentriert. Es wurde 1925 gegründet, als ein Wissenschaftskomitee die Notwendigkeit einer zentralisierten Sammlung biologischer Materialien erkannte, die Wissenschaftlern auf der ganzen Welt dienen könnten.
Die MRC-5-Zelllinie stammt aus normalem Lungengewebe eines 14 Wochen alten männlichen Fötus und wurde im September 1966 von JP Jacobs in ATCC hinterlegt. Es wird erklärt, dass sich diese Zellen vor dem Altern von 42 auf 46 Populationen verdoppeln können. beginnt. Der Referenzartikel für diese Zelllinie stammt aus dem Jahr 1970: https://www.nature.com/articles/227168a0
Die Ergebnisse
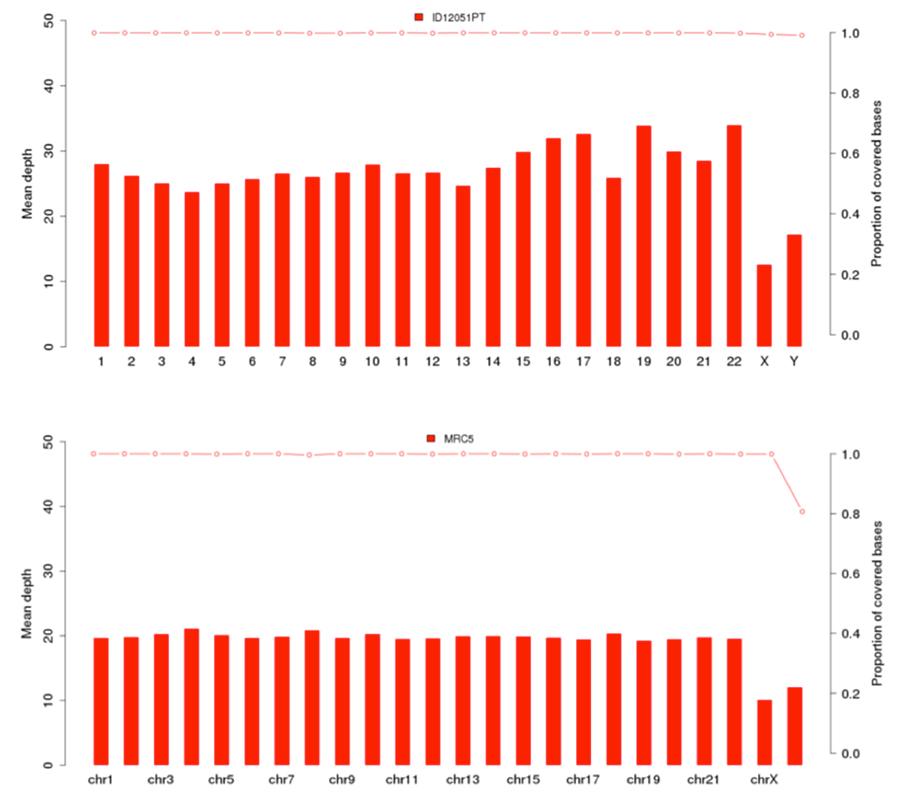
Wie zuvor gezeigt, ist die menschliche DNA in der Priorix Tetra®-Charge vorhanden. n. A71CB256A (in den folgenden Diagrammen als "Probe ID12051PT" angegeben) ist ein vollständiges individuelles Genom, dh die genomische DNA aller Chromosomen eines männlichen Individuums ist vorhanden. Die Abdeckungsgraphen (mittlere Tiefe = durchschnittliche Abdeckung) der 22 menschlichen Chromosomen und der X- und Y-Chromosomen sind unten für den Impfstoff (Bild oben) und die MRC5-Zelllinie (Bild unten) gezeigt.
Nachfolgend sind die Ergebnisse der Analyse der verschiedenen Arten von Varianten aufgeführt.
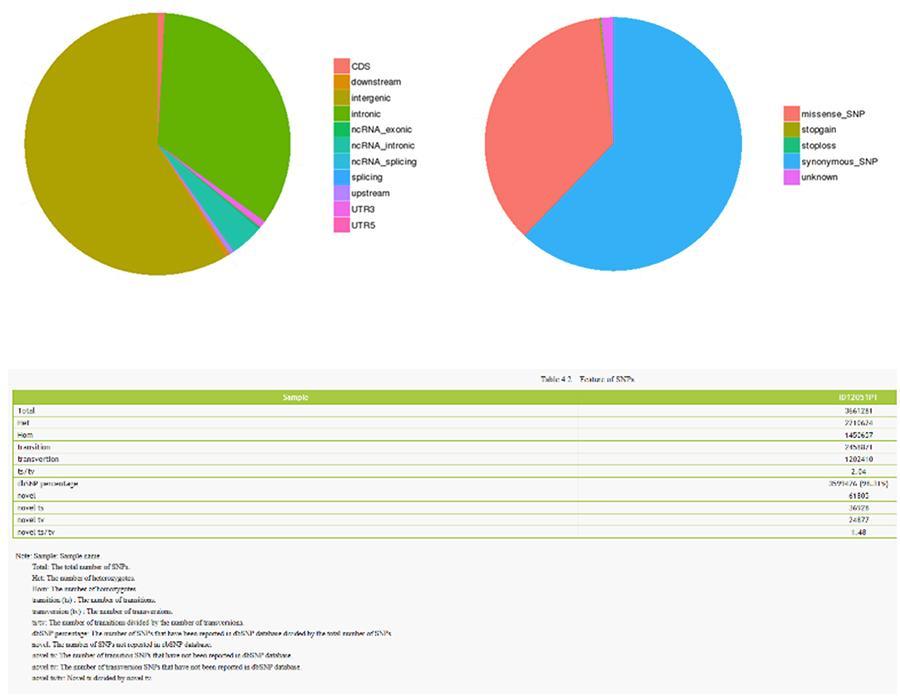
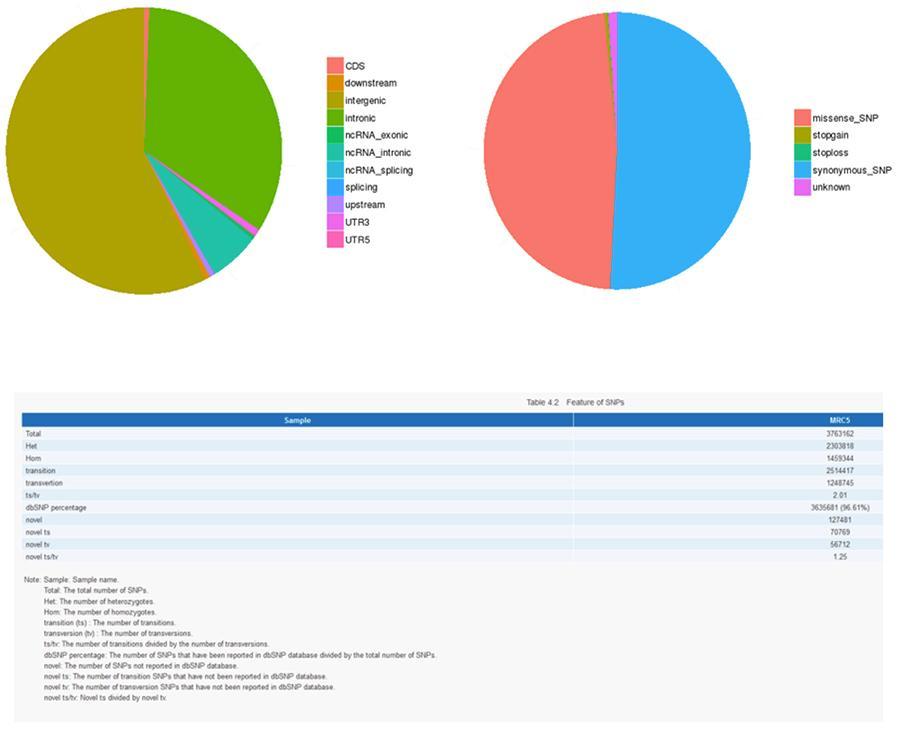
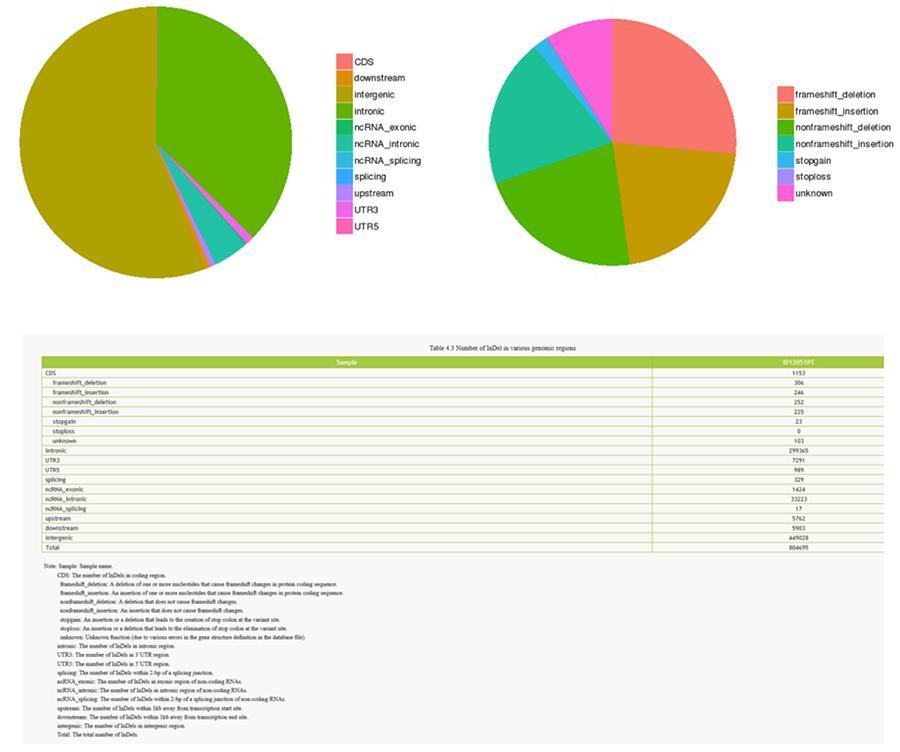
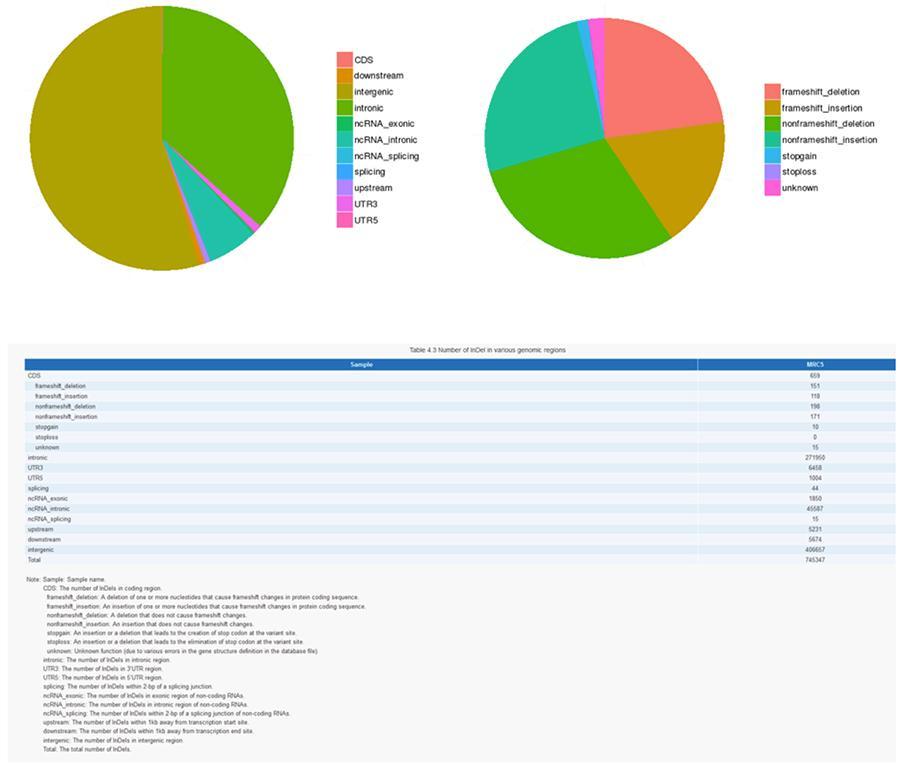
Einzelnukleotidpolymorphismus (SNP) und kurze Insertionen / Deletionen (InDels)
Die Varianten der einzelnen DNA (SNP, ausgesprochen "snip") sind Polymorphismen, dh Variationen des genetischen Materials, die von einem einzelnen Nukleotid getragen werden. Die 'InDels' sind kleine Insertionen und Deletionen mit einer Länge von weniger als 50 bp und bilden eine weitere Klasse genomischer Varianten im menschlichen Genom.
SNP (Einzelnukleotidpolymorphismus) - ID12051PT
SNP (Einzelnukleotidpolymorphismus) - MRC-5
InDels (kurze Einfügungen / Löschungen) - ID12051PT
InDels (kurze Einfügungen / Löschungen) - MRC-5
CNV (Copy Number Variants) und SV (Structural Variants)
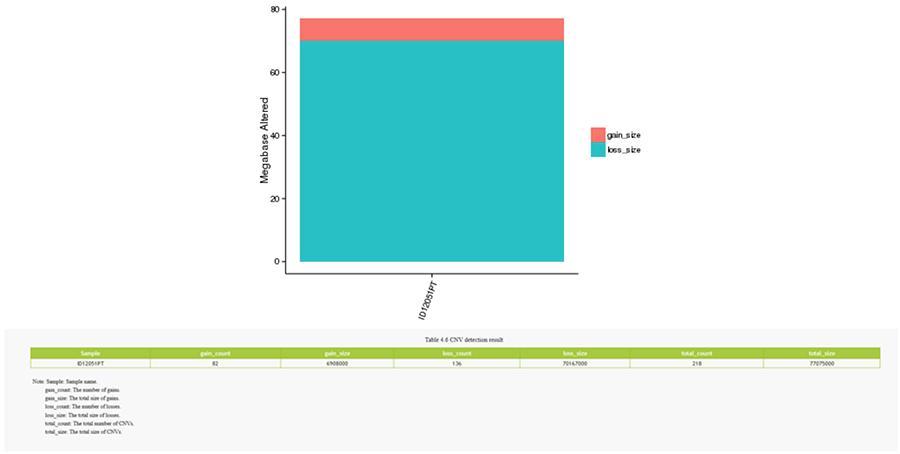
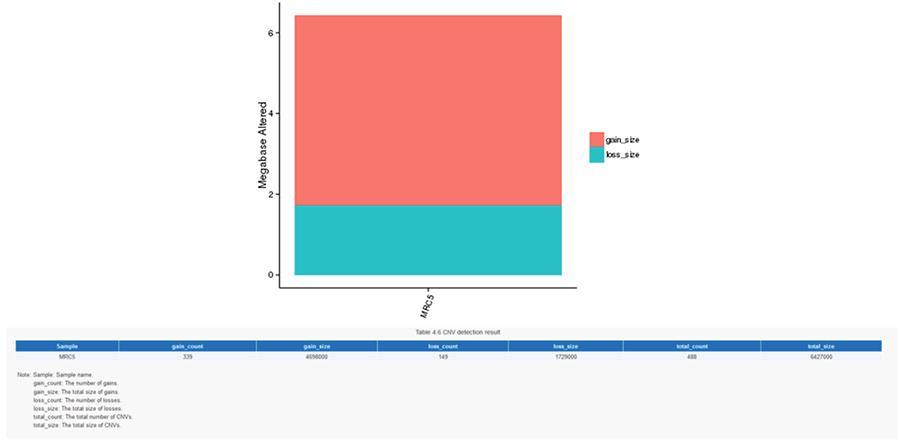
Kopienzahlvarianten (CNV) sind genomische Varianten aufgrund von Variationen in der Anzahl der Kopien relativ großer Fragmente (länger als 50 bp) in einzelnen Genomen. Es gibt zwei Arten von CNV: den Typ "Gewinn" (Kopiengewinn) und den Typ "Verlust" (Kopienverlust).
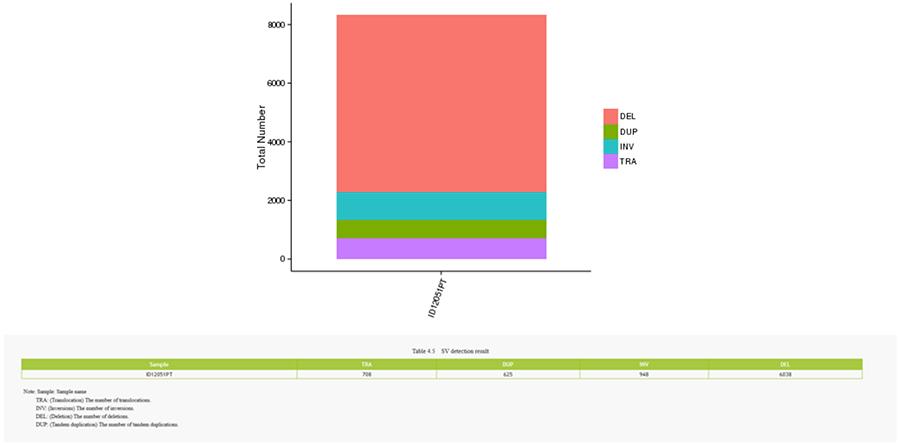
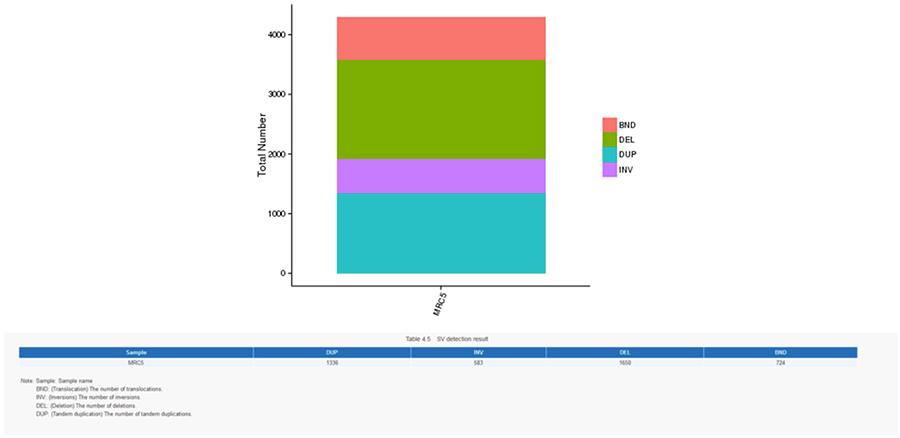
Strukturvarianten (SV) sind genomische Varianten mit relativ großen Dimensionen (> 50 bp), einschließlich Deletionen, Duplikationen, Insertionen, Invertierungen und Translokationen.
CNV (Kopienzahlvarianten)
SV (Strukturvarianten)
Zirkuläre Visualisierung von Genomen (Circos Plot)
Eine grafische Darstellung der beiden genannten Genome (Circos Plot) ist unten dargestellt.
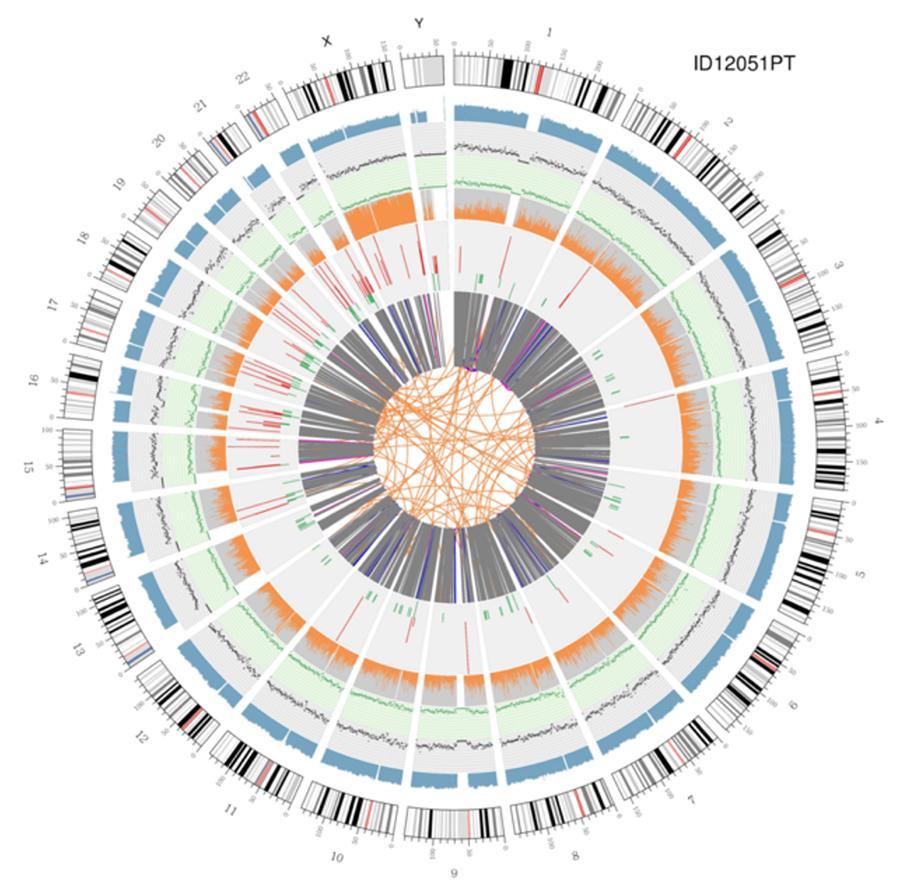
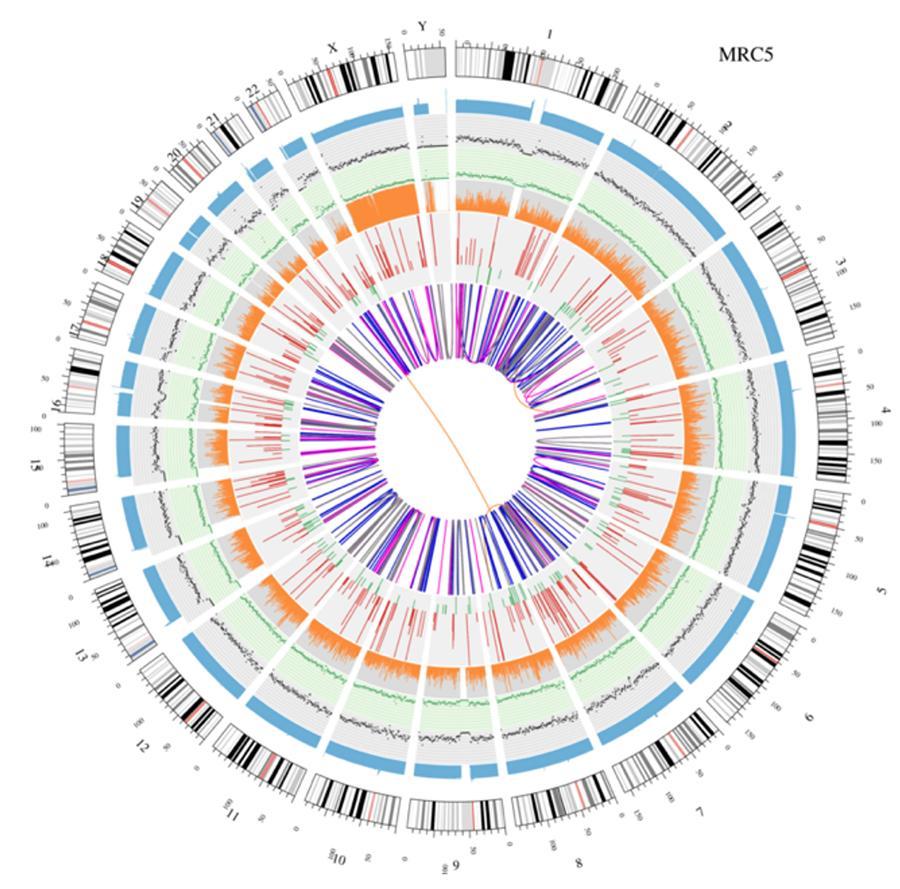
Bedeutung der verschiedenen konzentrischen Kreise
- Der äußere Kreis (erster Kreis) ist die Chromosomenzahl.
- Der zweite Ring (blau) repräsentiert die Abdeckung von Lesevorgängen im Hystogrammstil. Jedes Hystogramm ist die durchschnittliche Abdeckung einer Fläche von 0,5 Mbit / s.
- Der dritte Ring (schwarz) repräsentiert die Dichte der INDELs in einem "Dispersionsgraphenstil". Jeder Schwarzpunkt wird als Anzahl der INDELs (kleine Einfügungen / Löschungen) in einem Bereich von 1 Mbit / s berechnet.
- Der vierte Ring (grün) repräsentiert die snp-Dichte in einem "Dispersionsgraphenstil". Jeder grüne Punkt wird als Anzahl von SNPs (Einzelnukleotidpolymorphismen) in einem Bereich von 1 Mbit / s berechnet.
- Der fünfte Ring repräsentiert den Anteil von homozygotem (orange) und heterozygotem (grauem) SNP im Histogrammstil. Jedes Histogramm wird aus einer 1-Mbit / s-Region berechnet.
- Der sechste Ring repräsentiert die CNV-Inferenz (Kopienzahlvarianten). Rot bedeutet DNA-Stücke gewinnen und Grün bedeutet Verlust.
- Der zentralste Ring repräsentiert die SV-Inferenz (Strukturvarianten) in den exonischen und Spleißbereichen. TRA (Translokation, Orange), INS (Insertionen, Grün), DEL (Deletionen, Grau), DUP (Duplikationen, Pink) und INV (Inversionen, Blau).
Schlussfolgerungen
Diese beiden Genome zeigen wichtige Unterschiede. Insbesondere stellt sich heraus, dass das Impfstoffgenom im Vergleich zu dem der 1966 hinterlegten Zelllinie stark verändert ist. Es ist zu sagen, dass wir nicht die Möglichkeit hatten, die Sequenzierung der von GlaxoSmithKline für die Herstellung von verwendeten Zelllinie durchzuführen der Priorix Tetra®-Impfstoff, aber der des ursprünglichen Bestandes. Pharmaunternehmen, die Zelllinien zur Herstellung von Arzneimitteln und Impfstoffen verwenden, haben ihre eigene MRC-5-Linie. Dies ändert jedoch nichts an unserem Verdacht, dh die Tatsache, dass die Kontrolle der genetischen Stabilität nicht regelmäßig erforderlich ist, ist unserer Meinung nach sehr ernst. vor allem, weil es ohne Grenzschwelle vorhanden sein darf.
Schlussfolgerungen
Die beiden Genome zeigen wichtige Unterschiede. Insbesondere das Impfstoffgenom ist im Vergleich zu dem der 1966 hinterlegten Zelllinie stark verändert. Es muss gesagt werden, dass wir nicht die Möglichkeit hatten, die Zelllinie zu sequenzieren, die von GlaxoSmithKline für die Herstellung des Priorix Tetra-Impfstoffs verwendet wird, sondern die des Bestandes Original. Pharmaunternehmen, die Zelllinien zur Herstellung von Arzneimitteln und Impfstoffen verwenden, haben ihre MRC-5-Linie, aber dies ändert nichts an unserem Verdacht, dh der Tatsache, dass keine genetische Stabilitätskontrolle in regelmäßigen Abständen erforderlich ist, und dies ist unserer Meinung nach sehr ernst , vor allem, weil es unbegrenzt präsent sein darf.

